我国主栽水稻品种的育种亲本来源较为单一,遗传多样性匮乏[1
我国云南及与其接壤的缅甸、老挝等国同为亚洲栽培稻的起源地,这些区域稻种资源的主要性状及多样性程度备受关注。缅甸和老挝等国地处低纬度热带或亚热带季风气候区,具有海拔低、温度高和热量充足的特点,十分适宜水稻尤其是籼稻品种的种植与生长。缅甸素有“稻米之国”之称,是世界第七大稻谷生产国[15];水稻亦是老挝的主要农作物,其种植面积约占全国农作物种植总面积的85%[16],且当地稻种资源中不乏抗病虫和耐贫瘠等优异特性品种,是丰富和提高我国稻作资源多样性的理想引种来源。以往,我国从印度、日本和韩国等国引进的稻种资源较多,而从缅甸和老挝等国引进并加以利用的相对较少。目前,鲜见关于我国云南及与其相邻的缅甸和老挝稻种资源多样性比较分析的研究报道。
1 材料与方法
1.1 试验材料
参试材料共376份。包括与我国云南西双版纳州相邻的老挝琅南塔省当地水稻品种133份;缅甸北部掸邦、钦邦和克钦邦的水稻地方品种56份,以及缅甸其他来源地的水稻品种67份;我国云南西双版纳、普洱、德宏、临沧、保山和怒江6个边境州市当前水稻生产中种植利用的地方品种120份,详见网络增强出版附加材料附表1。为便于研究,将上述3个不同来源地的稻种资源分别命名为“老挝分析单元”、“缅甸分析单元”和“中国云南分析单元”。
1.2 DNA提取与SSR扩增
1.3 田间种植与表型性状观测
于云南省西双版纳景洪市嘎洒镇州农业科学研究所试验基地(20°57′22″ N,100°45′43″ E)进行田间种植并开展性状测定。该地属亚热带季风气候,年均气温21.7 ℃,年降水量1209.3 mm,年均日照时数1692.7 h,海拔580.0 m。于当地晚稻季7月中旬播种,8月初移栽,每份材料插栽2行,每行20苗,行距20 cm、株距13 cm,田间管理按当地生产习惯进行。参照《水稻种质资源描述规范和数据标准》[23],观测株高、穗长、有效穗数、穗粒数、穗实粒数、穗秕粒数、结实率、千粒重、穗抽出度、剑叶长和剑叶宽11个主要农艺性状。因13份材料种植后未收回种子,故共测定363份材料的表型性状。
1.4 数据统计与分析
在凝胶电泳图中,将有条带记为“1”,无带记为“0”。数据经转化后,运用Popgene 32软件计算3个分析单元稻种资源的多态位点数(number of polymorphic loci,NPL)、多态位点百分率(percentage of polymorphic loci,PPL)、等位基因数(number of alleles,Na)、有效等位基因数(number of effective alleles,Ne)、基因多样性指数(Neiʼs gene diversity,H)和多样性信息指数(Shannonʼs information index,I)6个遗传信息参数。对6个参数在3个分析单元的排名赋予相应分值,排名第一得3分、第二得2分、第三得1分,若排名相同则赋予相同分值。各分析单元6个参数的得分之和为该单元的遗传多样性综合得分,以此作为评估各分析单元遗传多样性丰富程度的依据。采用NTSYSpc软件计算遗传相似系数,采用MEGA 6.0软件进行聚类分析。
参照张海萍等[24]的方法,使用SPSS 24软件分析分子标记与表型性状值之间的相关性,利用该软件的一般线性模型(GLM)分析分子标记与表型观测值的回归关系,用回归方程的决定系数(R2)评估标记对表型变异的作用大小,即标记可解释的表型性状观测值变化百分率(P),公式为:P(%)=R2×100,并计算回归分析的测验值(F)。用SPSS 24软件的方差分析模型分析表型性状值在标记呈现不同带型时等位变异类型间的差异性。采用主成分分析进行优异资源筛选,使用SPSS 24软件进行观测原始数据标准化,按特征值≥1提取出主成分,使用Excel 2016计算特征向量和主成分综合得分。主成分综合得分计算公式:D=λ1/(λ1+λ2+λ3+λ4)×D1+…+λ4/(λ1+λ2+λ3+λ4)×D4,式中,D、λ、D1、…、D4分别表示主成分综合得分、特征值、第1至第4主成分得分。参试材料的主成分综合得分越高,说明其表型性状的综合表现越好。
2 结果与分析
2.1 3个分析单元稻种资源的遗传多样性
27对SSR标记在376份稻种资源中共检测到142个等位基因或等位变异位点,每个标记平均检测到的等位基因数为5.26个,检测到等位基因数最多的标记是RM3466,达11个,其次是RM1986(9个)、RM434(8个)和RM7097(7个)。
2.1.1 稻种资源的遗传多样性分析
表1结果显示,中国云南分析单元稻种资源的6项指标值均高于缅甸和老挝分析单元,说明其稻种资源遗传多样性较老挝和缅甸分析单元更为丰富,而老挝和缅甸分析单元基本相当。对各分析单元遗传多样性指标值的得分进行排序,3个分析单元参试稻种资源的遗传多样性综合得分从大到小依次为中国云南分析单元>缅甸分析单元>老挝分析单元。
表1 3个分析单元稻种资源的遗传多样性指标及得分
Table 1
| 分析单元 Analysis unit | 等位基因数 Na | 有效等位基因数 Ne | 基因多样性指数 H | Shannon多样性指数 I | 多态位点数 NPL | 多态位点百分率 PPL (%) | 得分 Score |
|---|---|---|---|---|---|---|---|
| 老挝Laos | 1.8803±0.3258 | 1.2424±0.3224 | 0.1526±0.1672 | 0.2510±0.2295 | 125 | 88.03 | 8 |
| 缅甸Myanmar | 1.9014±0.2992 | 1.2306±0.2847 | 0.1526±0.1538 | 0.2555±0.2141 | 128 | 90.14 | 11 |
| 中国云南Yunnan, China | 1.9437±0.2314 | 1.2487±0.2587 | 0.1704±0.1420 | 0.2871±0.1969 | 134 | 94.37 | 18 |
2.1.2 稀有等位变异位点与特有等位变异位点分析
在检测到的142个等位变异位点中,频率在5.0%及以下的稀有等位变异位点共100个,老挝、缅甸和中国云南分析单元分别有62、59和49个;3个分析单元中同时出现的稀有等位变异位点共19个,如RM1812A、B、C和RM3855A、C、D、G(表2)。在老挝与缅甸分析单元、老挝与中国云南分析单元和缅甸与中国云南分析单元之间同时出现的稀有等位变异位点分别为30、33和26个。仅在单个分析单元中出现的特有等位变异位点共9个,分别为中国云南分析单元的RM551A、RM214D、RM214H、RM1986G和缅甸分析单元的RM574A、RM434A、RM3643E、RM5481F、RM15090C,未在老挝分析单元中发现特有等位变异位点。综上,缅甸和老挝稻种资源中可挖掘利用的等位变异位点较我国云南稻种资源更为丰富,但我国云南与缅甸稻种资源的特有等位变异位点数相近。
表2 稀有等位变异、特有等位变异及其在3个分析单元中的分布
Table 2
| 标记 Marker | 稀有等位变异位点Rare allelic variation loci | 特有等位变异位点Peculiar allelic variation loci | |||||
|---|---|---|---|---|---|---|---|
| 老挝 Laos | 缅甸 Myanmar | 中国云南 Yunnan, China | 老挝 Laos | 缅甸 Myanmar | 中国云南 Yunnan, China | ||
| RM1812 | A、B、C、D | A、B、C、D、E | A、B、C | ||||
| RM574 | B | A | A | ||||
| RM551 | B、E | B、E | A、E | A | |||
| RM434 | B | A、B | B | A | |||
| RM214 | A、B、C、F | A、C、E、F | A、C、E、F、H | D、H | |||
| RM202 | A、F | B、C | B | ||||
| RM7097 | C、D | C、D | D | ||||
| RM3395 | A、D、E、G | A、D、G | A、D、E、G | ||||
| RM241 | A、D | D | |||||
| RM10806 | B | ||||||
| RM8004 | A、D | C | A | ||||
| RM471 | A、B、D | E | D | ||||
| RM1986 | A、B | A、B、C、D、E | A、B、G、H | G | |||
| RM3466 | A、D | C | A、D | ||||
| RM3525 | D | E | |||||
| RM3643 | C、D、F、I、J、K | C、D、E、I、J | C、F | E | |||
| RM3855 | A、B、C、D、E、G | A、C、D、F、G | A、C、D、G | ||||
| RM5481 | A、B、D | E、F | C、D | F | |||
| RM5611 | A、D | C | B | ||||
| RM6089 | B、C | D | C | ||||
| RM3394 | B、D、E | A、B、D、F、G | A、B、E、G | ||||
| RM7396 | A、D | E | A、B、D、E | ||||
| RM7390 | B、F | F | A、B、C | ||||
| RM8268 | A、B | A、D、E | E | ||||
| RM15090 | B、C | C | |||||
| RM3421 | A、D | D | A | ||||
| RM7479 | A | ||||||
2.1.3 基于SSR标记的聚类分析
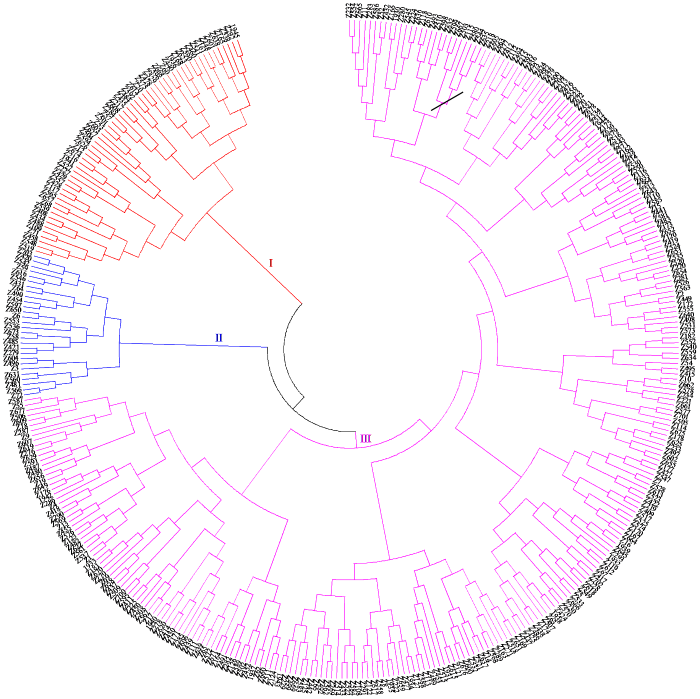
计算遗传相似系数并进行聚类分析,376份稻种资源可分为3个类群,类群Ⅰ、Ⅱ和Ⅲ分别包含59、28和289份(图1)。类群Ⅰ和Ⅱ共占总参试稻种资源的23.1%,类群Ⅲ占比达76.9%,数量最多。每一类群均含有3个分析单元的参试材料,即各分析单元的稻种资源关系较为复杂,可能存在民间种子交流行为。
图1
图1
基于SSR遗传相似系数的376份稻种资源聚类分析
Fig.1
Cluster analysis of 376 rice germplasm resources based on SSR genetic similarity coefficient
2.2 SSR标记与水稻表型性状的关系
2.2.1 SSR标记与表型性状的关联分析
SSR标记与表型性状的关联分析(表3)表明,27对SSR标记的不同等位变异与11个表型性状观测值之间存在不同程度的相关性,20对SSR标记(RM574、RM434、RM551、RM214、RM7097、RM202、RM1812、RM241、RM1086、RM8004、RM3466、RM3643、RM3855、RM5481、RM5611、RM6089、RM3394、RM7390、RM1509和RM7479)与多个表型性状有明显的相关性。
表3 SSR标记等位变异与水稻表型性状的相关系数
Table 3
| 标记 Marker | 等位 变异 Allelic variation | 有效穗数 Effective panicle number per plant | 株高 Plant height (cm) | 穗长 Panicle length (cm) | 穗抽出度 Panicle exsertion (cm) | 剑叶长 Flag leaf length (cm) | 剑叶宽 Flag leaf width (cm) | 穗实粒数 Filled grain number per panicle | 穗秕粒数 Unfilled grain number per panicle | 穗粒数 Grains per panicle | 结实率 Seed setting rate (%) | 千粒重 1000-grain weight (g) | ||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| RM574 | A | -0.092 | 0.098 | -0.064 | 0.161** | -0.025 | -0.015 | -0.191** | -0.003 | -0.145** | -0.124* | 0.041 | ||||
| B | -0.002 | -0.100 | 0.078 | -0.122* | 0.121* | 0.115* | 0.210** | -0.053 | 0.129* | 0.166** | -0.025 | |||||
| C | 0.093 | 0.015 | -0.045 | -0.014 | -0.123* | -0.118* | -0.090 | 0.073 | -0.027 | -0.096 | 0.005 | |||||
| RM434 | A | 0.093 | -0.115* | -0.060 | -0.070 | -0.080 | -0.090 | -0.020 | -0.010 | -0.030 | -0.000 | -0.060 | ||||
| B | -0.076 | 0.086 | 0.077 | 0.019 | 0.137* | -0.002 | 0.040 | -0.035 | 0.011 | 0.045 | 0.042 | |||||
| C | -0.176** | -0.024 | -0.179** | 0.178** | -0.153** | 0.026 | -0.291** | -0.159** | -0.313** | -0.010 | 0.225** | |||||
| D | 0.190** | 0.022 | 0.164** | -0.163** | 0.111* | -0.007 | 0.268** | 0.173** | 0.303** | -0.012 | -0.225** | |||||
| RM551 | A | 0.101 | 0.019 | -0.012 | -0.032 | -0.078 | -0.002 | -0.058 | -0.011 | -0.051 | -0.037 | -0.048 | ||||
| B | -0.095 | -0.079 | -0.357** | 0.329** | -0.272** | -0.251** | -0.362** | -0.226** | -0.405** | -0.029 | 0.118* | |||||
| C | -0.093 | 0.008 | 0.045 | 0.079 | 0.081 | -0.043 | 0.007 | -0.049 | -0.021 | 0.057 | 0.015 | |||||
| D | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||||
| E | 0.029 | 0.080 | 0.066 | -0.064 | 0.062 | -0.029 | 0.005 | -0.041 | -0.020 | 0.040 | 0.022 | |||||
| RM214 | A | -0.063 | -0.038 | -0.070 | 0.165** | 0.000 | 0.010 | -0.044 | -0.099 | -0.090 | 0.059 | 0.093 | ||||
| B | -0.128* | -0.117* | -0.279** | 0.163** | -0.240** | -0.178** | -0.246** | -0.190** | -0.293** | 0.061 | 0.061 | |||||
| C | -0.183** | -0.078 | -0.148** | 0.126* | -0.040 | -0.005 | -0.264** | -0.144** | -0.284** | 0.000 | 0.272** | |||||
| D | -0.045 | 0.004 | -0.171** | 0.158** | -0.217** | -0.110* | -0.254** | -0.144** | -0.275** | -0.019 | 0.073 | |||||
| E | 0.031 | 0.045 | -0.021 | 0.162** | -0.096 | -0.054 | -0.079 | -0.048 | -0.088 | -0.048 | -0.031 | |||||
| F | 0.031 | 0.011 | 0.015 | 0.081 | 0.076 | -0.020 | 0.043 | -0.054 | 0.001 | 0.080 | 0.061 | |||||
| G | 0.185** | 0.058 | 0.328** | -0.415** | 0.219** | 0.186** | 0.476** | 0.340** | 0.555** | -0.032 | -0.273** | |||||
| H | -0.010 | 0.148** | 0.126* | 0.057 | 0.148** | 0.041 | -0.096 | 0.000 | -0.074 | -0.076 | 0.020 | |||||
| RM7097 | A | -0.198** | -0.145** | -0.121* | -0.355** | 0.052 | 0.095 | -0.236** | -0.128* | -0.251** | 0.047 | -0.098 | ||||
| B | -0.211** | 0.138* | -0.069 | 0.188** | 0.018 | 0.009 | -0.188** | -0.138* | -0.221** | 0.011 | 0.182** | |||||
| C | 0.090 | 0.010 | -0.119* | -0.181** | -0.110* | -0.155** | -0.134* | 0.060 | -0.068 | -0.146** | -0.159** | |||||
| D | -0.093 | 0.014 | 0.009 | 0.222** | -0.044 | -0.078 | 0.033 | -0.059 | -0.009 | 0.036 | -0.008 | |||||
| RM202 | A | -0.189** | -0.037 | -0.114* | 0.126* | -0.038 | -0.060 | -0.117* | -0.161** | -0.181** | 0.120* | 0.252** | ||||
| B | -0.129* | -0.016 | -0.064 | 0.167** | 0.013 | -0.016 | -0.101 | -0.147** | -0.161** | 0.083 | 0.218** | |||||
| C | -0.020 | -0.023 | -0.261** | 0.153** | -0.275** | -0.185** | -0.266** | -0.113* | -0.267** | -0.093 | -0.064 | |||||
| D | -0.084 | 0.008 | 0.049 | -0.086 | -0.041 | 0.084 | 0.025 | 0.135* | 0.098 | -0.097 | 0.047 | |||||
| E | 0.078 | -0.201** | 0.146** | -0.179** | 0.099 | -0.021 | 0.095 | 0.039 | 0.094 | 0.004 | 0.054 | |||||
| F | 0.064 | -0.004 | -0.059 | 0.105 | -0.044 | 0.011 | -0.087 | -0.105 | -0.126* | 0.061 | -0.017 | |||||
| RM1812 | A | 0.059 | 0.067 | 0.086 | -0.133* | 0.080 | 0.060 | 0.081 | 0.129* | 0.135* | -0.078 | -0.158** | ||||
| B | 0.068 | -0.032 | 0.093 | -0.053 | 0.081 | 0.066 | 0.096 | 0.053 | 0.104 | 0.005 | 0.038 | |||||
| C | -0.134* | -0.002 | -0.024 | -0.002 | 0.051 | -0.033 | -0.077 | 0.031 | -0.041 | -0.055 | -0.032 | |||||
| D | -0.026 | -0.051 | -0.321** | 0.191** | -0.262** | -0.187** | -0.285** | -0.154** | -0.306** | -0.040 | 0.008 | |||||
| E | -0.126* | -0.037 | -0.132* | 0.190** | -0.119* | -0.102 | -0.216** | -0.156** | -0.253** | 0.028 | 0.162** | |||||
| F | 0.151** | -0.063 | 0.121* | -0.073 | 0.078 | -0.010 | 0.120* | 0.057 | 0.125* | 0.027 | -0.076 | |||||
| RM3395 | A | 0.064 | 0.056 | -0.038 | -0.012 | 0.021 | -0.026 | 0.005 | 0.145** | 0.086 | -0.098 | -0.047 | ||||
| B | 0.106 | -0.140* | -0.057 | -0.043 | 0.024 | -0.052 | -0.106 | 0.061 | -0.047 | -0.142* | 0.017 | |||||
| C | 0.019 | 0.118* | 0.027 | 0.088 | -0.093 | -0.093 | 0.074 | -0.069 | 0.019 | 0.077 | -0.200** | |||||
| D | -0.246** | 0.005 | -0.002 | 0.019 | 0.015 | 0.039 | -0.090 | -0.101 | -0.126* | 0.059 | 0.211** | |||||
| E | 0.062 | -0.006 | -0.090 | 0.076 | -0.039 | -0.002 | -0.066 | 0.068 | -0.011 | -0.039 | -0.018 | |||||
| F | 0.015 | 0.087 | 0.183** | -0.116* | 0.056 | 0.132* | 0.106 | 0.003 | 0.082 | 0.049 | 0.044 | |||||
| G | -0.073 | -0.128* | -0.170** | 0.067 | 0.015 | 0.022 | 0.071 | -0.092 | 0.002 | 0.134* | 0.053 | |||||
| RM241 | A | 0.016 | 0.093 | 0.078 | 0.089 | 0.057 | 0.041 | -0.075 | 0.064 | -0.021 | -0.013 | -0.079 | ||||
| B | 0.073 | -0.286** | -0.142* | -0.026 | -0.268** | -0.131* | -0.228** | -0.041 | -0.198** | -0.092 | -0.087 | |||||
| C | -0.028 | 0.116* | 0.055 | -0.076 | 0.154** | 0.098 | 0.217** | 0.027 | 0.180** | 0.063 | 0.038 | |||||
| D | -0.094 | 0.185** | 0.060 | 0.076 | 0.124* | 0.034 | 0.085 | -0.042 | 0.043 | 0.056 | 0.175** | |||||
| RM1086 | A | -0.255** | -0.060 | -0.198** | 0.260** | -0.147** | -0.010 | -0.416** | -0.233** | -0.447** | -0.022 | 0.377** | ||||
| B | -0.020 | -0.127* | -0.348** | 0.256** | -0.275** | -0.280** | -0.297** | -0.020 | -0.237** | -0.168** | -0.090 | |||||
| RM8004 | A | -0.255** | -0.058 | -0.198** | 0.260** | -0.147** | -0.013 | -0.416** | -0.233** | -0.447** | -0.002 | 0.377** | ||||
| B | -0.021 | -0.127* | -0.348** | 0.256** | -0.275** | -0.280** | -0.297** | -0.019 | -0.237** | -0.168** | -0.086 | |||||
| C | 0.037 | -0.018 | -0.159** | 0.164** | -0.096 | -0.064 | -0.084 | -0.060 | -0.099 | 0.030 | 0.037 | |||||
| D | -0.176** | -0.036 | -0.246** | 0.244** | -0.176** | -0.133* | -0.285** | -0.162** | -0.310** | -0.011 | 0.224** | |||||
| E | 0.186** | 0.058 | 0.214** | -0.180** | 0.167** | 0.093 | 0.297** | 0.152** | 0.313** | 0.025 | -0.178** | |||||
| F | -0.076 | -0.038 | 0.102 | -0.101 | 0.031 | 0.094 | -0.025 | -0.015 | -0.028 | 0.011 | -0.008 | |||||
| RM471 | A | 0.078 | 0.048 | 0.107 | -0.004 | 0.022 | -0.013 | 0.056 | 0.064 | 0.080 | -0.002 | -0.018 | ||||
| B | -0.069 | 0.175** | -0.165** | 0.130* | -0.113 | -0.005 | -0.060 | -0.080 | -0.092 | 0.029 | 0.004 | |||||
| C | 0.022 | -0.003 | 0.011 | 0.066 | 0.109 | -0.076 | -0.049 | -0.151* | -0.125* | 0.063 | 0.160** | |||||
| D | 0.064 | 0.063 | -0.043 | -0.071 | 0.023 | 0.080 | -0.005 | 0.228** | 0.127* | -0.164** | -0.171** | |||||
| E | -0.051 | -0.227** | 0.096 | -0.156** | -0.054 | 0.057 | 0.081 | 0.080 | 0.110 | -0.004 | -0.085 | |||||
| RM1986 | A | -0.037 | 0.042 | -0.112 | 0.159** | -0.145* | -0.027 | -0.122* | 0.073 | -0.052 | -0.107 | -0.056 | ||||
| B | -0.111 | 0.061 | -0.062 | 0.012 | 0.008 | 0.238** | 0.117* | -0.017 | 0.080 | 0.053 | 0.139* | |||||
| C | -0.111 | 0.061 | -0.062 | 0.012 | 0.008 | 0.238** | 0.117* | -0.017 | 0.080 | 0.053 | 0.139* | |||||
| D | -0.034 | -0.174** | -0.003 | -0.126* | -0.072 | 0.059 | 0.042 | -0.066 | -0.006 | 0.105 | 0.083 | |||||
| E | 0.009 | 0.084 | 0.059 | 0.099 | 0.101 | 0.003 | 0.066 | -0.071 | 0.009 | 0.105 | 0.136* | |||||
| F | 0.046 | -0.101 | 0.062 | 0.074 | -0.060 | -0.189** | -0.075 | -0.094 | -0.113 | 0.026 | -0.123* | |||||
| RM3466 | A | -0.020 | -0.208** | -0.346** | 0.104 | -0.117* | -0.110 | -0.040 | -0.146* | -0.110 | 0.168** | 0.049 | ||||
| B | -0.226** | -0.040 | -0.155** | 0.268** | -0.144* | -0.040 | -0.380** | -0.195** | -0.404** | -0.030 | 0.276** | |||||
| C | 0.181** | 0.039 | 0.241** | 0.289** | 0.113 | 0.034 | 0.346** | 0.236** | 0.402** | -0.060 | -0.272** | |||||
| D | 0.048 | 0.200** | 0.138* | 0.031 | 0.132* | 0.112 | -0.020 | -0.060 | -0.050 | 0.020 | 0.067 | |||||
| RM3525 | A | 0.079 | 0.151* | 0.130* | -0.040 | 0.236** | 0.089 | 0.124* | 0.115 | 0.161** | -0.060 | -0.143* | ||||
| B | -0.060 | 0.022 | -0.142* | -0.030 | -0.100 | -0.070 | -0.050 | -0.110 | -0.110 | 0.065 | 0.071 | |||||
| C | -0.121* | -0.080 | 0.004 | -0.002 | -0.030 | -0.010 | -0.060 | -0.060 | -0.080 | -0.010 | 0.073 | |||||
| D | -0.080 | 0.157** | -0.040 | 0.140* | -0.126* | 0.029 | -0.020 | 0.048 | 0.015 | -0.100 | -0.003 | |||||
| E | -0.040 | 0.127* | -0.050 | 0.075 | -0.030 | 0.042 | -0.050 | 0.133* | 0.040 | -0.050 | 0.090 | |||||
| RM3643 | A | 0.180** | -0.196** | 0.171** | -0.208** | 0.103 | 0.092 | 0.248** | 0.090 | 0.243** | 0.043 | -0.090 | ||||
| B | -0.090 | 0.202** | 0.136* | -0.159** | 0.073 | 0.144* | 0.211** | 0.052 | 0.192** | 0.076 | 0.017 | |||||
| C | -0.040 | 0.241** | 0.135* | -0.030 | 0.237** | -0.003 | 0.159** | 0.214** | 0.245** | -0.080 | -0.206** | |||||
| D | -0.100 | -0.020 | 0.058 | -0.010 | 0.031 | 0.005 | -0.070 | 0.006 | -0.050 | -0.020 | 0.075 | |||||
| E | 0.228** | -0.386** | -0.060 | -0.178** | -0.127* | -0.050 | 0.115 | 0.036 | 0.110 | 0.009 | -0.155** | |||||
| F | -0.050 | 0.244** | 0.077 | 0.016 | 0.057 | 0.081 | 0.073 | 0.033 | 0.074 | 0.038 | 0.042 | |||||
| G | 0.013 | 0.241** | 0.056 | 0.087 | 0.136* | -0.060 | 0.038 | 0.095 | 0.084 | -0.060 | -0.177** | |||||
| H | -0.020 | -0.010 | -0.080 | 0.095 | -0.110 | -0.050 | -0.268** | -0.090 | -0.258** | -0.110 | 0.114 | |||||
| I | -0.309** | 0.052 | -0.010 | 0.126* | 0.042 | 0.103 | -0.135* | -0.166** | -0.199** | 0.101 | 0.331** | |||||
| RM3855 | A | -0.273** | 0.205** | 0.067 | 0.204** | 0.096 | 0.060 | 0.036 | -0.070 | -0.020 | 0.098 | 0.092 | ||||
| B | -0.030 | 0.004 | -0.030 | -0.020 | -0.040 | 0.004 | 0.030 | -0.080 | -0.020 | 0.013 | 0.109 | |||||
| C | 0.031 | -0.100 | -0.163** | 0.067 | -0.151* | -0.204** | -0.228** | -0.169** | -0.273** | 0.016 | -0.030 | |||||
| D | -0.040 | -0.030 | -0.002 | 0.075 | -0.030 | -0.050 | -0.020 | -0.127* | -0.090 | 0.118* | 0.129* | |||||
| E | 0.041 | -0.040 | -0.170** | 0.171** | -0.144* | -0.040 | -0.260** | -0.128* | -0.273** | -0.010 | 0.068 | |||||
| F | 0.176** | -0.050 | 0.202** | -0.321** | 0.154** | 0.114 | 0.237** | 0.319** | 0.364** | -0.146* | -0.185** | |||||
| G | 0.107 | -0.117* | -0.149* | 0.034 | -0.100 | -0.129* | -0.050 | -0.070 | -0.080 | 0.087 | -0.110 | |||||
| RM5481 | A | -0.259** | -0.002 | -0.123* | 0.149* | -0.090 | 0.010 | -0.267** | -0.175** | -0.307** | -0.030 | 0.334** | ||||
| B | -0.100 | -0.136* | -0.310** | 0.331** | -0.245** | -0.251** | -0.347** | -0.238** | -0.401** | -0.001 | 0.137* | |||||
| C | 0.044 | -0.117* | -0.362** | 0.166** | -0.359** | -0.313** | -0.245** | -0.118* | -0.256** | -0.026 | -0.151* | |||||
| D | 0.050 | 0.230** | 0.112 | -0.030 | 0.097 | 0.056 | 0.229** | 0.150* | 0.262** | 0.014 | -0.187** | |||||
| E | 0.166** | -0.040 | 0.315** | -0.349** | 0.243** | 0.214** | 0.308** | 0.205** | 0.353** | 0.006 | -0.125* | |||||
| RM5611 | A | 0.078 | -0.070 | -0.249** | 0.253** | -0.276** | -0.295** | -0.305** | -0.110 | -0.296** | -0.070 | -0.060 | ||||
| B | -0.030 | -0.060 | -0.010 | 0.011 | 0.067 | -0.010 | 0.091 | -0.010 | 0.066 | 0.057 | -0.040 | |||||
| C | -0.060 | 0.058 | 0.173** | -0.266** | 0.108 | 0.193** | 0.074 | 0.146* | 0.142* | -0.090 | 0.026 | |||||
| D | 0.051 | 0.009 | -0.080 | 0.192** | -0.030 | -0.030 | 0.015 | -0.154** | -0.080 | 0.173** | 0.081 | |||||
| RM6089 | A | -0.151* | -0.138* | -0.409** | 0.342** | -0.281** | -0.269** | -0.407** | -0.271** | -0.469** | 0.015 | 0.140* | ||||
| B | -0.134* | -0.020 | 0.020 | 0.046 | 0.002 | 0.011 | -0.010 | -0.060 | -0.040 | 0.048 | 0.154** | |||||
| C | -0.030 | -0.002 | 0.002 | 0.036 | 0.069 | 0.050 | 0.012 | -0.010 | 0.005 | 0.021 | 0.018 | |||||
| D | 0.173** | 0.124* | 0.352** | -0.329** | 0.205** | 0.204** | 0.349** | 0.252** | 0.414** | -0.030 | -0.163** | |||||
| RM3394 | A | 0.093 | -0.070 | -0.070 | 0.043 | -0.090 | -0.100 | -0.060 | 0.022 | -0.030 | -0.050 | -0.185** | ||||
| B | 0.116* | -0.177** | -0.040 | -0.001 | -0.030 | -0.040 | -0.010 | -0.050 | -0.040 | 0.042 | 0.021 | |||||
| C | 0.112 | -0.403** | -0.149* | -0.050 | -0.137* | -0.232** | -0.060 | -0.206** | -0.164** | 0.153** | 0.004 | |||||
| D | -0.164** | -0.010 | -0.100 | 0.190** | -0.145* | 0.002 | -0.297** | -0.120* | -0.298** | -0.080 | 0.158** | |||||
| E | -0.060 | -0.110 | -0.222** | 0.098 | -0.060 | -0.030 | -0.137* | -0.070 | -0.144* | 0.074 | 0.128* | |||||
| F | -0.050 | 0.305** | 0.288** | -0.131* | 0.233** | 0.149* | 0.185** | 0.219** | 0.269** | -0.118* | -0.020 | |||||
| G | 0.009 | 0.046 | 0.069 | -0.010 | 0.089 | 0.035 | -0.004 | -0.030 | -0.020 | 0.033 | 0.029 | |||||
| RM7396 | A | 0.058 | -0.080 | -0.110 | 0.020 | -0.080 | -0.080 | -0.040 | -0.050 | -0.060 | 0.068 | -0.070 | ||||
| B | -0.123* | 0.067 | 0.045 | -0.060 | 0.128* | 0.096 | 0.095 | 0.117* | 0.140* | -0.050 | -0.127* | |||||
| C | 0.036 | -0.070 | -0.010 | -0.060 | -0.080 | 0.022 | -0.080 | -0.050 | -0.090 | -0.060 | 0.180** | |||||
| D | 0.055 | 0.041 | 0.005 | 0.140* | -0.010 | -0.110 | 0.052 | -0.050 | 0.012 | 0.127* | -0.080 | |||||
| RM7390 | A | -0.040 | -0.060 | -0.189** | 0.028 | -0.213** | -0.050 | -0.200** | -0.080 | -0.198** | -0.050 | -0.050 | ||||
| B | -0.148* | 0.037 | 0.043 | 0.086 | 0.090 | -0.002 | 0.016 | -0.090 | -0.040 | 0.098 | 0.085 | |||||
| C | -0.080 | 0.082 | -0.030 | 0.132* | -0.050 | 0.008 | -0.144* | -0.135* | -0.189** | 0.041 | 0.204** | |||||
| D | -0.040 | -0.080 | -0.237** | 0.253** | -0.110 | -0.133* | -0.197** | -0.070 | -0.190** | -0.010 | 0.131* | |||||
| E | -0.158** | -0.117* | -0.256** | 0.080 | -0.238** | -0.143* | -0.360** | -0.040 | -0.300** | -0.167** | 0.096 | |||||
| F | 0.117* | 0.123* | 0.049 | 0.047 | 0.061 | -0.030 | 0.002 | 0.017 | 0.011 | -0.010 | -0.119* | |||||
| RM8268 | A | -0.020 | 0.110 | 0.117* | -0.100 | 0.051 | 0.074 | -0.010 | 0.045 | 0.015 | -0.070 | 0.135* | ||||
| B | -0.030 | -0.030 | -0.120 | 0.083 | -0.040 | -0.060 | -0.157** | -0.050 | -0.151* | -0.010 | 0.000 | |||||
| C | -0.133* | 0.030 | -0.119* | 0.127* | -0.030 | 0.031 | -0.195** | -0.040 | -0.169** | -0.070 | 0.163** | |||||
| D | 0.004 | 0.222** | 0.197** | -0.080 | 0.057 | 0.122* | 0.234** | 0.130* | 0.253** | 0.010 | -0.110 | |||||
| E | 0.166** | -0.340** | -0.070 | -0.050 | 0.001 | -0.139* | 0.058 | -0.110 | -0.020 | 0.154** | -0.070 | |||||
| RM1509 | A | -0.333** | -0.090 | -0.225** | 0.222** | -0.110 | -0.110 | -0.321** | -0.227** | -0.400** | 0.074 | 0.360** | ||||
| B | 0.353** | -0.030 | 0.152* | -0.262** | 0.045 | 0.038 | 0.232** | 0.081 | 0.231** | -0.001 | -0.230** | |||||
| C | -0.110 | 0.234** | 0.111 | 0.127 | 0.122 | 0.134* | 0.127 | 0.266** | 0.279** | -0.139* | -0.205** | |||||
| RM3421 | A | -0.090 | -0.010 | 0.003 | 0.107 | 0.008 | 0.137* | -0.197** | -0.130 | -0.207** | -0.020 | 0.259** | ||||
| B | -0.030 | -0.010 | -0.100 | 0.130 | -0.168* | 0.025 | -0.100 | -0.100 | -0.120 | 0.094 | 0.039 | |||||
| C | 0.158* | -0.110 | 0.048 | -0.207** | 0.135 | -0.110 | 0.181** | 0.135 | 0.197** | -0.060 | -0.163* | |||||
| D | -0.120 | 0.155* | 0.014 | 0.059 | 0.011 | 0.025 | -0.030 | -0.020 | -0.030 | -0.030 | 0.009 | |||||
| RM7479 | A | -0.030 | -0.156* | -0.470** | 0.426** | -0.384** | -0.338** | -0.363** | -0.228** | -0.418** | 0.023 | -0.040 | ||||
| B | -0.204** | 0.019 | -0.243** | 0.139* | -0.175** | -0.070 | -0.319** | -0.181** | -0.356** | -0.050 | 0.311** | |||||
| C | 0.183** | 0.078 | 0.527** | -0.421** | 0.403** | 0.299** | 0.532** | 0.305** | 0.596** | 0.039 | -0.217** | |||||
“*”和“**”分别表示差异显著(P < 0.05)和极显著(P < 0.01)。下同。
“*”and“**”indicate significant difference (P < 0.05) and extremely significant difference (P < 0.01), respectively. The same below.
RM1086有2个等位变异,A类型与有效穗数、穗长和剑叶长等6个性状呈极显著负相关,与千粒重呈极显著正相关;B类型与株高、穗长、剑叶长和剑叶宽等7个性状呈显著或极显著负相关,与穗抽出度呈极显著正相关。RM5841有5个等位变异,A类型与有效穗数、穗长和穗实粒数等5个性状呈显著负相关,与穗抽出度和千粒重呈显著正相关;C类型显著关联到9个性状,其中,与千粒重呈显著负相关;E类型也显著关联到9个性状;D类型关联到的性状数最少,为5个。RM6089有4个等位变异,A和D类型共同显著关联到10个性状,但作用相反;B和C类型关联的性状数较少或无显著关联。RM1509有3个等位变异,A、B和C类型分别显著关联7、6和6个性状。RM7479有3个等位变异,A、B和C类型分别显著关联8、8和9个性状。
7对SSR标记(RM3395、RM471、RM1986、RM3525、RM7396、RM8268和RM3421)与表型性状相关性较弱。RM3395有7个等位变异,最多能与3个性状显著关联,其中E类型与所有观测性状均无显著相关性。RM471有5个等位变异,每个类型显著关联的性状数均在4个以下,其中A类型与所有观测性状均无明显关联。RM1986有6个等位变异,最多能与3个性状有明显的相关性。RM3525有5个等位变异,只有A类型能显著关联到株高、穗长和剑叶长等5个性状,其他4个等位变异只能显著关联到1或2个性状。RM7396有4个等位变异,除B类型与5个性状关联外,其他3个等位变异显著关联的性状数较少。RM8268有5个等位变异,除C和D类型分别与6个性状显著关联外,其他3个等位变异显著关联的性状数较少。RM3421有4个等位变异,但能显著关联的性状最多为5个。
SSR标记可解释的性状观测值变化(表4)表明,27对标记可解释性状的观测值变化为0.0%~ 33.5%。其中,RM214、RM1086、RM5481、RM6089、RM1509和RM7479共6对标记可解释多个性状观测值的变化百分率在10.0%及以上,F值达到极显著,对性状影响作用较大;RM202、RM8004、RM3466、RM3855和RM3394等5对标记可解释多个性状值的变化百分率在5.0%~ 10.0%,这些标记均与性状关联性紧密;其余标记可解释的性状观测值变化比例均较小。
表4 分子标记解释的水稻性状观测值变化百分率
Table 4
| 标记 Marker | 指标 Index | 有效穗数 Effective panicle number per plant | 株高 Plant height | 穗长 Panicle length | 穗抽出度 Panicle exsertion | 剑叶长 Flag leaf length | 剑叶宽 Flag leaf width | 穗实粒数 Filled grain number per panicle | 穗秕粒数 Unfilled grain number per panicle | 穗粒数 Grains per panicle | 结实率 Seed- setting rate | 千粒重 1000-grain weight | ||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| RM574 | P (%) | 1.4 | 0.3 | 0.0 | 1.2 | 0.4 | 0.5 | 0.4 | 0.3 | 0.5 | 0.0 | 0.1 | ||||||
| F | 4.602* | 0.859 | 0.034 | 3.934* | 1.393 | 1.533 | 1.141 | 0.802 | 1.684 | 0.061 | 0.169 | |||||||
| RM434 | P (%) | 2.2 | 0.0 | 1.6 | 1.5 | 0.6 | 0.0 | 4.8 | 2.3 | 6.5 | 0.0 | 3.2 | ||||||
| F | 7.018** | 0.159 | 5.267* | 4.886* | 1.950 | 0.098 | 16.157** | 7.618** | 22.132** | 0.100 | 10.519** | |||||||
| RM551 | P (%) | 0.0 | 0.5 | 2.4 | 2.0 | 1.9 | 0.4 | 2.4 | 0.6 | 2.5 | 0.2 | 0.1 | ||||||
| F | 0.100 | 1.389 | 7.224** | 5.940* | 5.752* | 1.208 | 7.227** | 1.857 | 7.496** | 0.589 | 0.245 | |||||||
| RM214 | P (%) | 5.3 | 2.3 | 16.5 | 13.1 | 8.6 | 3.4 | 19.3 | 11.1 | 27.4 | 0.6 | 7.2 | ||||||
| F | 17.655** | 7.498** | 62.736** | 48.014** | 29.888** | 11.036** | 75.928** | 39.613** | 119.915** | 1.772 | 24.803** | |||||||
| RM7097 | P (%) | 2.2 | 1.1 | 1.3 | 16.0 | 0.8 | 2.3 | 3.3 | 0.9 | 3.6 | 0.3 | 0.0 | ||||||
| F | 7.199** | 3.606 | 4.131* | 61.081** | 2.690 | 7.422** | 10.845** | 2.850 | 12.109** | 1.126 | 0.030 | |||||||
| RM202 | P (%) | 8.2 | 0.3 | 4.1 | 6.5 | 1.2 | 0.7 | 4.3 | 3.9 | 7.4 | 0.8 | 8.2 | ||||||
| F | 18.939** | 0.720 | 8.923** | 14.640** | 2.511 | 1.518 | 9.435** | 8.492** | 16.801** | 1.647 | 18.829** | |||||||
| RM1812 | P (%) | 0.1 | 0.1 | 0.0 | 0.2 | 0.1 | 0.1 | 0.1 | 0.4 | 0.0 | 0.6 | 0.4 | ||||||
| F | 0.227 | 0.411 | 0.040 | 0.627 | 0.216 | 0.234 | 0.147 | 1.248 | 0.115 | 1.783 | 1.062 | |||||||
| RM3395 | P (%) | 0.9 | 0.1 | 0.2 | 0.0 | 0.1 | 1.6 | 1.2 | 0.8 | 0.1 | 2.6 | 0.8 | ||||||
| F | 2.962 | 0.198 | 0.546 | 0.043 | 0.304 | 5.248* | 3.941* | 2.495 | 0.413 | 8.522** | 2.676 | |||||||
| RM241 | P (%) | 0.8 | 3.0 | 0.2 | 0.0 | 2.7 | 0.4 | 5.0 | 0.2 | 2.2 | 0.7 | 3.3 | ||||||
| F | 2.717 | 9.882** | 0.774 | 0.148 | 8.870** | 1.370 | 16.722** | 0.485 | 7.280** | 2.340 | 10.809** | |||||||
| RM1086 | P (%) | 3.0 | 4.0 | 7.0 | 2.3 | 5.0 | 10.1 | 0.9 | 2.8 | 0.1 | 3.5 | 17.4 | ||||||
| F | 2.855 | 3.873 | 6.914** | 2.194 | 4.839* | 10.356** | 0.873 | 2.684 | 0.102 | 3.379 | 19.356** | |||||||
| RM8004 | P (%) | 0.4 | 0.0 | 8.8 | 8.6 | 3.3 | 2.9 | 5.1 | 1.7 | 6.1 | 0.0 | 3.0 | ||||||
| F | 1.391 | 0.065 | 30.779** | 30.042** | 10.879** | 9.507** | 17.004** | 5.511* | 20.581** | 0.002 | 9.794** | |||||||
| RM471 | P (%) | 0.1 | 5.0 | 0.4 | 2.7 | 0.0 | 0.4 | 0.2 | 1.0 | 0.9 | 0.2 | 0.8 | ||||||
| F | 0.359 | 15.082** | 1.139 | 7.830** | 0.011 | 1.164 | 0.704 | 2.863 | 2.709 | 0.580 | 2.195 | |||||||
| RM1986 | P (%) | 1.7 | 1.1 | 2.6 | 0.0 | 0.4 | 8.8 | 0.3 | 2.2 | 1.3 | 0.7 | 1.2 | ||||||
| F | 3.742 | 2.449 | 5.735* | 0.006 | 0.777 | 20.559** | 0.654 | 4.868* | 2.900 | 1.501 | 2.669 | |||||||
| RM3466 | P (%) | 2.8 | 5.8 | 15.7 | 5.4 | 4.7 | 2.0 | 6.4 | 4.4 | 9.9 | 1.0 | 3.4 | ||||||
| F | 8.187** | 17.371** | 52.774** | 16.042** | 13.904** | 5.729* | 19.361** | 13.041** | 31.221** | 2.863 | 9.829* | |||||||
| RM3525 | P (%) | 1.1 | 0.1 | 0.7 | 1.7 | 3.5 | 0.0 | 1.0 | 0.3 | 0.2 | 0.3 | 1.6 | ||||||
| F | 2.640 | 0.199 | 1.513 | 3.895* | 8.213** | 0.000 | 2.425 | 0.604 | 0.562 | 0.664 | 3.796 | |||||||
| RM3643 | P (%) | 1.2 | 0.3 | 1.3 | 2.6 | 0.5 | 0.3 | 4.2 | 0.8 | 4.7 | 0.0 | 1.2 | ||||||
| F | 5.961* | 1.667 | 6.535* | 13.156** | 2.244 | 1.271 | 21.812** | 4.119* | 24.060** | 0.181 | 5.955* | |||||||
| RM3855 | P (%) | 7.1 | 2.1 | 0.3 | 6.2 | 0.1 | 0.1 | 0.7 | 5.2 | 3.8 | 1.5 | 3.4 | ||||||
| F | 21.356** | 5.929* | 0.729 | 18.638** | 0.190 | 0.311 | 2.013 | 15.242** | 11.111** | 4.336* | 9.789** | |||||||
| RM5481 | P (%) | 6.8 | 0.4 | 13.4 | 15.0 | 8.3 | 4.7 | 21.1 | 9.2 | 27.7 | 0.0 | 9.0 | ||||||
| F | 20.714** | 1.179 | 43.844** | 49.916** | 25.590** | 13.936** | 75.681** | 28.778** | 108.266** | 0.127 | 29.119** | |||||||
| RM5611 | P (%) | 0.0 | 0.7 | 2.2 | 1.0 | 2.2 | 4.2 | 3.1 | 0.0 | 2.0 | 1.0 | 1.0 | ||||||
| F | 0.097 | 1.922 | 6.295* | 2.712 | 6.217* | 12.165** | 8.916** | 0.021 | 5.605* | 2.765 | 2.965 | |||||||
| RM6089 | P (%) | 3.1 | 2.0 | 16.4 | 12.7 | 7.0 | 6.6 | 16.3 | 7.9 | 22.3 | 0.1 | 2.8 | ||||||
| F | 9.133** | 5.681* | 55.593** | 41.220** | 21.420** | 19.910** | 55.326** | 24.219** | 81.372** | 0.200 | 8.145** | |||||||
| RM3394 | P (%) | 2.2 | 21.5 | 6.5 | 0.5 | 6.2 | 5.7 | 2.6 | 4.6 | 6.5 | 1.0 | 0.3 | ||||||
| F | 5.851* | 69.705** | 17.672** | 1.344 | 16.917** | 15.346** | 6.927** | 12.299** | 17.670** | 2.612 | 0.882 | |||||||
| RM7396 | P (%) | 0.6 | 0.0 | 0.1 | 1.1 | 0.2 | 0.6 | 0.0 | 0.6 | 0.3 | 0.4 | 0.5 | ||||||
| F | 1.655 | 0.124 | 0.247 | 3.146 | 0.466 | 1.648 | 0.024 | 1.611 | 0.718 | 1.162 | 1.388 | |||||||
| RM7390 | P (%) | 2.8 | 0.1 | 0.1 | 0.7 | 0.3 | 0.4 | 0.1 | 4.1 | 2.8 | 1.6 | 3.2 | ||||||
| F | 2.435 | 0.066 | 0.123 | 0.568 | 0.258 | 0.354 | 0.118 | 3.592 | 2.358 | 1.376 | 2.710 | |||||||
| RM8268 | P (%) | 2.2 | 3.7 | 0.0 | 0.4 | 0.0 | 0.5 | 4.2 | 0.0 | 2.1 | 2.2 | 3.0 | ||||||
| F | 6.450* | 10.727** | 0.109 | 1.175 | 0.026 | 1.537 | 12.482** | 0.135 | 5.960* | 6.410* | 8.572** | |||||||
| RM1509 | P (%) | 5.8 | 3.4 | 6.0 | 1.8 | 2.4 | 2.5 | 11.3 | 10.1 | 22.3 | 1.6 | 16.3 | ||||||
| F | 13.739** | 8.035** | 14.418** | 4.165* | 5.427* | 5.742* | 28.569** | 25.198** | 64.646** | 3.719 | 43.945** | |||||||
| RM3421 | P (%) | 0.1 | 0.6 | 0.3 | 1.4 | 1.0 | 0.8 | 2.7 | 1.8 | 3.3 | 0.3 | 3.5 | ||||||
| F | 0.139 | 1.217 | 0.685 | 2.883 | 1.942 | 1.709 | 5.564* | 3.589 | 6.861** | 0.648 | 7.239** | |||||||
| RM7479 | P (%) | 1.8 | 1.8 | 31.9 | 22.2 | 20.1 | 12.4 | 26.1 | 9.4 | 33.5 | 0.0 | 1.6 | ||||||
| F | 4.203* | 4.203* | 105.892** | 64.563** | 56.990** | 32.023** | 79.993** | 23.362** | 113.933** | 0.010 | 3.648 | |||||||
2.2.2 表型性状在SSR标记等位变异间的差异
部分表型性状在SSR标记不同等位变异间存在显著差异(表5)。标记RM7479的等位变异在8个表型性状上表现出差异,其3个等位变异A、B和C对应的穗长分别为短(20.352 cm)、中(22.730 cm)和长(25.712 cm),剑叶长分别为短(23.981 cm)、中(27.842 cm)和长(31.825 cm),穗抽出度分别为长(8.782 cm)、中(5.372 cm)和短(3.010 cm),且差异均达显著水平;剑叶宽分为窄(1.385 cm)和宽(1.617、1.722 cm)2组,穗实粒数、穗秕粒数、穗粒数及千粒重亦表现为差异显著的2组。类似地,标记RM1509的等位变异在7个表型性状上存在显著差异;RM3466、RM5611、RM5481和RM202的等位变异分别在5个表型性状上表现出显著差异。RM7479、RM1509、RM3466、RM5481、RM202和RM3855这6对标记同时也是解释性状变异比例较高的标记。此外,虽然RM8004、RM6089和RM3394仅分别在2、2和1个性状上表现出等位变异间的显著差异,但对性状变异的解释比例较高。
表5 不同SSR标记等位变异间的水稻表型性状差异
Table 5
| 标记 Marker | 性状 Trait | 等位变异Allelic variation | ||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| A | B | C | D | E | F | G | ||||||||||
| RM574 | 穗抽出度(cm) | 5.110a | 3.634b | 3.869b | ||||||||||||
| 穗实粒数 | 93.568b | 118.674a | 104.204b | |||||||||||||
| RM1509 | 有效穗数 | 5.241b | 7.440a | 5.867b | ||||||||||||
| 株高(cm) | 114.975b | 121.514b | 158.033a | |||||||||||||
| 穗抽出度(cm) | 5.947a | 3.068b | 6.437a | |||||||||||||
| 剑叶宽(cm) | 1.623b | 1.710b | 1.917a | |||||||||||||
| 穗实粒数 | 87.827b | 126.353a | 151.822a | |||||||||||||
| 穗秕粒数 | 22.179b | 45.994b | 100.388a | |||||||||||||
| 穗粒数 | 110.006c | 172.432b | 252.210a | |||||||||||||
| RM7479 | 穗长(cm) | 20.352c | 22.730b | 25.712a | ||||||||||||
| 穗抽出度(cm) | 8.782a | 5.372b | 3.010c | |||||||||||||
| 剑叶长(cm) | 23.981c | 27.842b | 31.825a | |||||||||||||
| 剑叶宽(cm) | 1.385b | 1.617a | 1.722a | |||||||||||||
| 穗实粒数 | 64.971b | 75.195b | 122.804a | |||||||||||||
| 穗秕粒数 | 18.655b | 25.032b | 45.232a | |||||||||||||
| 穗粒数 | 83.627b | 100.258b | 168.135a | |||||||||||||
| 千粒重(g) | 26.833b | 30.986a | 26.695b | |||||||||||||
| RM7097 | 穗抽出度(cm) | 2.589c | 4.943b | 6.834ab | 8.553a | |||||||||||
| RM241 | 株高(cm) | 129.749ab | 113.999c | 126.473b | 136.312a | |||||||||||
| 剑叶长(cm) | 31.926a | 29.075b | 32.040a | 33.004a | ||||||||||||
| 千粒重(g) | 25.527b | 26.118b | 26.860b | 29.076a | ||||||||||||
| M3466 | 株高(cm) | 99.543c | 120.741b | 123.502b | 149.720a | |||||||||||
| 穗长(cm) | 20.051c | 23.708b | 25.318b | 27.194a | ||||||||||||
| 剑叶长(cm) | 27.916b | 28.890b | 31.283b | 34.952a | ||||||||||||
| 穗实粒数 | 105.561a | 72.997b | 120.944a | 107.380a | ||||||||||||
| 结实率(%) | 85.070a | 72.790b | 73.350b | 75.400b | ||||||||||||
| RM5611 | 穗长(cm) | 21.411b | 24.795a | 25.221a | 23.095a | |||||||||||
| 剑叶长(cm) | 23.825b | 31.995a | 31.293a | 30.354a | ||||||||||||
| 剑叶宽(cm) | 1.300b | 1.667a | 1.705a | 1.648a | ||||||||||||
| 穗实粒数 | 54.438b | 123.596a | 114.577a | 114.779a | ||||||||||||
| 穗粒数 | 79.724b | 163.798a | 158.224a | 139.047a | ||||||||||||
| RM6089 | 有效穗数 | 6.463a | 3.900b | 6.951a | 7.349a | |||||||||||
| 千粒重(g) | 28.211b | 35.575a | 27.028b | 26.250b | ||||||||||||
| RM8004 | 穗长(cm) | 21.460c | 23.502b | 25.444a | 25.987a | |||||||||||
| 穗抽出度(cm) | 8.813a | 5.957b | 3.494bc | 2.686c | ||||||||||||
| RM3421 | 穗实粒数 | 75.087b | 102.912a | 118.110a | 105.922a | |||||||||||
| 穗粒数 | 99.072b | 135.735a | 158.124a | 141.240a | ||||||||||||
| 千粒重(g) | 31.875a | 27.465b | 26.421b | 27.288b | ||||||||||||
| RM471 | 穗秕粒数 | 47.960b | 35.188b | 35.502b | 69.342a | 45.679b | ||||||||||
| 千粒重(g) | 26.393a | 26.739a | 27.525a | 23.495b | 25.918a | |||||||||||
| RM3525 | 剑叶长(cm) | 34.282a | 29.566b | 30.686b | 28.836b | 30.326b | ||||||||||
| RM5481 | 穗长(cm) | 23.661b | 22.484b | 15.225c | 25.802a | 25.686a | ||||||||||
| 剑叶长(cm) | 29.285ab | 27.415b | 13.325c | 32.358a | 32.039a | |||||||||||
| 剑叶宽(cm) | 1.681ab | 1.496b | 0.920c | 1.713a | 1.720a | |||||||||||
| 穗粒数 | 98.766b | 98.156b | 32.300c | 191.251a | 169.199a | |||||||||||
| 千粒重(g) | 31.803a | 28.320b | 20.558d | 24.384c | 26.218bc | |||||||||||
| RM8268 | 株高(cm) | 137.000a | 120.047b | 124.452ab | 128.778ab | 104.802c | ||||||||||
| RM202 | 穗长(cm) | 23.607a | 24.258a | 20.758b | 25.334a | 25.682a | 24.110a | |||||||||
| 剑叶长(cm) | 30.124a | 31.245a | 22.711b | 30.446a | 31.836a | 29.752a | ||||||||||
| 剑叶宽(cm) | 1.612a | 1.662a | 1.404b | 1.732a | 1.662a | 1.692a | ||||||||||
| 穗实粒数 | 92.390a | 95.910a | 52.414b | 114.300a | 118.600a | 94.130a | ||||||||||
| 穗粒数 | 112.411a | 118.741a | 73.673b | 164.907a | 160.624a | 118.331a | ||||||||||
| RM1812 | 穗长(cm) | 26.100a | 26.100a | 24.681ab | 21.746c | 23.894b | 25.330ab | |||||||||
| 千粒重(g) | 23.331b | 27.380a | 25.980a | 26.780a | 28.780a | 26.380a | ||||||||||
| RM1986 | 穗抽出度(cm) | 7.252a | 4.249bc | 4.249bc | 2.568c | 5.126b | 4.922b | |||||||||
| 剑叶长(cm) | 26.870b | 31.026a | 31.026a | 29.636a | 32.360a | 30.001a | ||||||||||
| RM3395 | 穗秕粒数 | 73.633a | 42.805bc | 36.777bc | 28.864c | 52.440b | 40.561bc | 27.626c | ||||||||
| RM3855 | 有效穗数 | 5.706c | 6.928bc | 7.363bc | 6.800bc | 7.398bc | 7.496b | 9.267a | ||||||||
| 株高(cm) | 136.477a | 123.272a | 114.501a | 120.412a | 119.928a | 121.798a | 94.000b | |||||||||
| 穗长(cm) | 25.443a | 24.607a | 23.144a | 24.865a | 23.281a | 25.514a | 20.307b | |||||||||
| 千粒重(g) | 27.848a | 28.396a | 26.214a | 29.181a | 27.679a | 25.833a | 21.453b | |||||||||
| RM3394 | 千粒重(g) | 21.730b | 27.043a | 26.728a | 29.020a | 29.013a | 26.546a | 27.890a | ||||||||
不同小写字母表示在P < 0.05水平差异显著。
Different lowercase letters indicate significant difference at P < 0.05 level.
2.3 表型性状的主成分分析及优异稻种资源筛选
对11个表型性状的主成分分析显示,特征值>1.000的主成分共4个,累计方差贡献率达77.218%(表6)。其中,PC1贡献率为34.510%,特征向量最大值对应穗粒数,其次为穗长、剑叶长、剑叶宽及穗实粒数,命名为叶穗因子;PC2贡献率为17.690%,特征向量最大值对应结实率,其次为穗秕粒数,命名为结实因子;PC3贡献率为13.251%,特征向量最大值对应有效穗数,命名为穗数因子;PC4贡献率为11.767%,特征向量最大值对应穗抽出度,其次为株高,命名为株高因子。
表6 稻种资源表型性状的主成分分析
Table 6
| 项目 Item | 主成分Principle component | |||
|---|---|---|---|---|
| PC1 | PC2 | PC3 | PC4 | |
| 株高Plant height (cm) | 0.247 | 0.108 | -0.372 | 0.606 |
| 穗长Panicle length (cm) | 0.400 | 0.126 | -0.095 | 0.101 |
| 有效穗数Effective panicle number per plant | -0.114 | -0.125 | 0.507 | 0.254 |
| 穗实粒数Filled grain number per panicle | 0.369 | 0.268 | 0.392 | 0.071 |
| 穗秕粒数Unfilled grain number per panicle | 0.306 | -0.537 | -0.080 | -0.008 |
| 穗粒数Grains per panicle | 0.455 | -0.103 | 0.252 | 0.051 |
| 结实率Seed setting rate (%) | -0.064 | 0.628 | 0.332 | 0.011 |
| 千粒重1000-grain weight (g) | 0.017 | 0.351 | -0.380 | -0.468 |
| 穗抽出度Panicle exsertion (cm) | -0.188 | 0.198 | -0.295 | 0.607 |
| 剑叶长Flag leaf length (cm) | 0.391 | 0.132 | -0.029 | 0.029 |
| 剑叶宽Flag leaf width (cm) | 0.370 | 0.109 | -0.171 | -0.211 |
| 特征值Eigenvalue | 3.796 | 1.946 | 1.458 | 1.294 |
| 方差贡献率Variance contribution rate (%) | 34.510 | 17.690 | 13.251 | 11.767 |
| 累计贡献率Cumulative contribution rate (%) | 34.510 | 52.200 | 65.451 | 77.218 |
基于363份材料的主成分综合得分排序,筛选出综合得分>1.000的优异种质36份(表7)。其中排名前3且得分>2.000的稻种分别为中国云南的花壳、毫糯浪及老挝的纳列5。花壳源自中国云南德宏州芒市,株高160 cm,穗粒数210,结实率85%,千粒重24 g,有效穗数11.4,穗长30 cm,属大穗型品种,可作为多穗大穗型亲本;毫糯浪源自中国云南德宏州芒市,株高142 cm,穗长约24 cm,有效穗数5.4,结实率90%,千粒重27 g,株高适中、糯性优良,可作为糯稻新品种选育的亲本;纳列5源自老挝琅南塔省,株高119 cm,穗长27 cm,穗抽出度1.3 cm,剑叶长37 cm、宽2.2 cm,有效穗数5.6,穗粒数310,可作为大穗型亲本。363份水稻材料的综合得分详见网络增强出版附加材料附表1。
表7 主成分综合得分≥1.000的稻种资源
Table 7
| 编号Code | 分析单元Analysis unit | 种质名称Germplasm name | PC1 | PC2 | PC3 | PC4 | D |
|---|---|---|---|---|---|---|---|
| Z7 | 中国云南 | 大白谷 | 2.385 | 1.095 | -0.282 | 2.361 | 1.628 |
| Z15 | 中国云南 | huoheng | 0.932 | 5.537 | -0.718 | 1.370 | 1.771 |
| Z21 | 中国云南 | 花壳 | 2.866 | 3.401 | 0.973 | 2.451 | 2.600 |
| Z25 | 中国云南 | 小勐卯 | 2.282 | -0.585 | 1.569 | 0.009 | 1.157 |
| Z30 | 中国云南 | 毫糯浪 | 0.078 | 8.905 | -0.693 | 0.838 | 2.084 |
| Z82 | 中国云南 | 黄板所 | 1.882 | 1.099 | 0.308 | -0.063 | 1.136 |
| Z107 | 中国云南 | 桂朝糯 | 1.667 | 1.559 | 0.299 | 0.557 | 1.238 |
| Z112 | 中国云南 | 红吊谷 | 2.336 | 0.581 | 0.745 | 2.510 | 1.687 |
| Z113 | 中国云南 | 绿帮谷 | 1.727 | 1.038 | 0.595 | 2.181 | 1.444 |
| Z143 | 老挝 | 纳列3 | 3.113 | 0.772 | 0.249 | -1.674 | 1.356 |
| Z162 | 老挝 | 纳列5 | 4.308 | -0.336 | 1.730 | -0.146 | 2.123 |
| Z163 | 老挝 | 纳列13 | 3.750 | 0.327 | -0.228 | -0.664 | 1.610 |
| Z170 | 老挝 | 曼岛9 | 2.126 | 2.077 | 0.050 | 1.961 | 1.733 |
| Z173 | 老挝 | 曼岛16 | 2.512 | 0.862 | -0.003 | 0.266 | 1.360 |
| Z194 | 老挝 | 纳列9 | 1.571 | 1.956 | -1.059 | 1.552 | 1.205 |
| Z211 | 老挝 | 南元Y10 | 2.240 | 0.576 | -0.406 | -0.415 | 1.000 |
| Z213 | 老挝 | 南元Y12 | 2.213 | 2.070 | 0.235 | -0.259 | 1.464 |
| Z232 | 老挝 | BLKS1176 | 1.926 | 1.997 | -0.336 | -0.983 | 1.111 |
| Z298 | 缅甸 | Ssin thukha | 1.984 | -1.077 | 1.880 | 0.650 | 1.062 |
| Z329 | 缅甸 | Naung Tu Mee She | 1.160 | 1.096 | 0.794 | 1.418 | 1.122 |
| Z339 | 缅甸 | Yakhine Bo | 2.925 | -0.637 | 1.196 | 1.038 | 1.524 |
| Z341 | 缅甸 | Kyun Put Gyi | 2.753 | -0.135 | -0.939 | 1.952 | 1.335 |
| Z342 | 缅甸 | Saba Phyu | 3.811 | -1.893 | -1.926 | 3.008 | 1.397 |
| Z343 | 缅甸 | Shwe Pyi Aye | 1.867 | 0.716 | 1.186 | 1.023 | 1.358 |
| Z347 | 缅甸 | Nga Hhmwe | 1.384 | 0.774 | 1.542 | 1.142 | 1.234 |
| Z349 | 缅甸 | Man Sar | 0.646 | 1.157 | 0.354 | 3.137 | 1.093 |
| Z351 | 缅甸 | Ta Yay Gyi | 2.033 | 2.333 | -1.360 | 3.814 | 1.791 |
| Z352 | 缅甸 | Kyaung Thwa | 3.682 | -1.981 | -0.973 | 2.669 | 1.431 |
| Z354 | 缅甸 | Mayin Ni | 1.874 | 0.799 | 0.394 | 0.156 | 1.112 |
| Z356 | 缅甸 | Lone Phyu | 2.838 | 0.173 | 1.218 | 0.561 | 1.602 |
| Z357 | 缅甸 | Let Thae Gyan | 2.531 | 1.097 | -1.089 | 3.505 | 1.729 |
| Z358 | 缅甸 | Myin Thwa Gyi | 2.001 | 0.870 | -0.357 | 0.848 | 1.162 |
| Z362 | 缅甸 | Saw Pha Gyi | 2.568 | 0.428 | -1.080 | 1.645 | 1.311 |
| Z363 | 缅甸 | Khao La Shae | 1.858 | 1.225 | -0.348 | 0.463 | 1.122 |
| Z364 | 缅甸 | Khaw Ma Kyaw | 3.820 | -1.353 | 0.393 | 0.778 | 1.583 |
| Z369 | 缅甸 | Ye Tha | 1.793 | 0.222 | 1.247 | 0.703 | 1.173 |
3 讨论
3.1 稻种资源的遗传多样性分析
3.2 SSR标记等位变异与表型性状关联分析
关联分析是解析复杂性状遗传基础的重要方法[29],相较于连锁作图等传统QTL定位方法,其具有更高的准确率与研究效率,可通过整合表型与基因多样性信息挖掘更多的功能性基因位点[30]。随着分子技术发展,采用关联分析开展表型性状与分子标记变异位点关系的研究日益增多,邹德堂等[31]利用SSR标记在108个水稻品种中定位出13个与4种功能成分含量性状显著相关的位点,并挖掘出29个相关优异等位基因及代表性载体材料;夏秀忠等[32]则通过34个SSR标记鉴定出1个同时与芽期和苗期耐冷性相关联的位点。本研究应用的27对SSR标记中,RM3395、RM471、RM1986、RM3525、RM7396、RM8268和RM3421共7对标记与观测性状的关联性较弱,其余20对标记与性状关联性密切,且能解释一定比例的性状变异。黎毛毛等[33]发现标记RM1812与11号染色体上RM1812~ RM332区间的碱消值QTL(qADV11)相关,本研究中RM1812的D和A等位变异可将穗长与剑叶长区分为差异明显的2类;方云霞[34]指出RM6089与叶卷缩基因rl10(t)连锁(遗传距离5.00 cm),本研究发现RM6089存在4个等位变异,其中A和D类型与除结实率外的10个性状呈显著或极显著相关,可解释穗长、穗抽出度、穗实粒数和穗粒数变异的12.7%~22.3%,以及剑叶长、剑叶宽和穗秕粒数变异的6.6%~7.9%。此外,RM7097的4个等位变异中,A类型与株高、穗长和穗抽出度呈显著或极显著负相关,与有效穗数、穗实粒数、穗秕粒数和穗粒数呈显著或极显著正相关,表明其可能与刘健等[35]发现降低株高的qPH3.1及提高籽粒产量的qGY3.2存在关联的研究结果一致。
3.3 优异资源筛选
种质资源是生物遗传信息的载体,蕴藏着抗性、品质和高产等相关基因,表型性状评价是挖掘优异基因、选育与改良品种的有效途径[36]。多性状研究中,性状数量多且存在相关性会导致观测值重叠,增加工作量,不利于高效鉴定。主成分分析通过降维将多个相关性状转化为少数的主成分,可识别关键指标、简化数据结构,更准确地反映农作物品种整体性能,提高评价的准确性与可靠性[37]。品种优良性需通过各性状协调平衡体现,利用主成分得分评价综合表现的方法已在种质资源评价中广泛应用[38
4 结论
利用27对SSR标记对我国云南边境地区3个分析单元的376份稻种资源遗传多样性进行分析,共检测到142个等位变异位点,其中100个为稀有等位变异位点;中国云南与缅甸分析单元共有9个特有等位变异位点。遗传多样性的6个参数综合得分排序为中国云南分析单元>缅甸分析单元>老挝分析单元。RM214、RM1086、RM5481、RM6089、RM1509和RM7479与表型性状关联密切,可解释穗长、穗抽出度、穗实粒数、穗秕粒数、穗粒数及千粒重等性状10.0%以上的变异。主成分分析提取到4个主成分,筛选出综合得分>2.000的优异种质花壳(中国云南)、纳列5(老挝)和毫糯浪(中国云南)。
参考文献
寒地超级稻龙粳31祖先亲本追溯及遗传基础解析
DOI:10.13430/j.cnki.jpgr.2016.03.005

龙粳31是黑龙江省农业科学院水稻研究所选育的寒地早粳超级稻新品种,具有早熟、高产、优质、抗病、抗倒、耐寒等诸多优点。本文对其亲本进行追溯,构建系谱图,分析亲本主要特性及核遗传贡献率,揭示其遗传演化历程,为水稻育种亲本的选择和利用提供参考。结果表明:龙粳31属于下北细胞质家族,传递途径为:下北→早丰→合江20→合江21→龙粳10号→龙粳13→龙粳31。核遗传物质由祖先亲本下北、石狩白毛、农林11、虾夷、笹锦、红星2号、奥羽239、曲系17、藤系117、雪光、越光、收921、空知、北明、空育125、北海84、台中27、高雄53、合选58和色江克按不同比例共同提供,核遗传贡献率分别为:4.6875%、0.9766%、2.5391%、8.2031%、3.9063%、3.1250%、3.9063%、7.8125%、15.6250%、1.5625%、1.5625%、3.1250%、6.2500%、12.5000%、0.7813%、0.7813%、0.7813%、6.2500%和3.1250%。亲本选择时,要注重母本在当地的适应性,而父本则应具有地理远缘或生态远缘的基因血缘;遗传基础狭窄是寒地稻区水稻育种取得新突破的主要限制因素。
基于SSR标记的高原粳稻品种遗传多样性分析
利用产量位点标记分析中国水稻骨干恢复系与南亚及东南亚恢复系的遗传多样性
DOI:10.13430/j.cnki.jpgr.2017.03.003
[本文引用: 2]

本研究利用47个根据已报道的QTL位点或者已被精细定位或克隆的与水稻产量性状基因紧密连锁的产量位点标记,对来自中国、印度和越南等国的58份水稻恢复系(其中,中国14份,印度18份,菲律宾3份,越南12份,孟加拉8份,泰国2份,韩国1份)进行遗传多样性分析。结果表明:(1)在中国恢复系中,47个功能基因标记中有36个具有多态性,共检测到90个等位基因,每个标记检测到等位基因2~4个,平均为2.500个;有效等位基因共62.905个,平均每个标记1.747个;36个有效标记的Shannon信息指数平均值为0.632,变幅为0.271~1.266。(2)在来自国外的材料中,47个功能基因标记均具有多态性,共检测到131个等位基因,每个标记检测到的等位基因数为2~6个,平均2.787个;有效等位基因数共82.686个,平均1.759个;47个标记的Shannon信息指数平均值为0.649,变幅为0.109~1.110。(3)聚类分析显示,在遗传相似系数为0.73水平上,参试资源聚为3大类群,中国资源多聚在第Ⅰ类群下的第1、2、3亚群,越南资源多聚在Ⅰ-4亚群,孟加拉资源多聚在第Ⅲ类群下的第3亚群。由此表明,中国资源遗传基础较为狭窄,而其他国家的恢复系具有较远的亲缘关系。
中国水稻地方品种与选育品种的遗传多样性比较分析
DOI:10.13430/j.cnki.jpgr.2015.03.001
[本文引用: 1]

本研究利用98对SSR标记对202份中国栽培稻地方种和选育种的遗传多样性进行比较分析。结果显示供试品种具有较丰富的遗传多样性,共检测到等位基因1350个,每个位点的等位基因数(Na)变化范围为3-39,平均14个;Nei基因多样性指数变化范围(He)为0.125-0.955,平均0.733;多态信息量(PIC)变化范围为0.122-0.953,平均0.680;稀有等位基因数(Nr)913个;等位基因丰度(Rs)8.33。栽培稻地方种和选育种遗传多样性差异明显,地方种等位基因数、Nei基因多样性指数、多态信息量、稀有等位基因数和等位基因丰度(Na=1219,He=0.747,PIC=0.710,Nr=756,Rs=8.50)均高于选育种(Na=919,He=0.704,PIC=0.650,Nr=529,Rs=7.01)。各染色体组水平的遗传多样性分析表明,选育种仅在1号染色体上的遗传多样性高于地方种,进一步分析显示选育种的遗传改良在基因组水平上具有区间特异性。
Analysis of genetic diversity and population structure of rice cultivars from Korea, China and Japan using SSR markers
东南亚62个籼型水稻亲本SSR遗传多样性分析
DOI:10.11869/j.issn.100-8551.2016.05.0859
[本文引用: 1]

为探讨东南亚水稻亲本间的遗传多样性,以东南亚62份籼型水稻亲本为材料,选择29对水稻功能基因标记以及平均分布于12条染色体、多态性较高和条带清晰的72对SSR引物进行遗传多样性和聚类分析。结果表明,32对多态性引物在62份水稻材料中检测到201个等位基因,每个位点等位基因数(Na)变异范围为2~12,平均为6.281;有效等位基因数(Ne)变异范围为1.067~5.399,平均为2.867;多态信息含量(PIC)变异范围为0.061~0.789,平均为0.515;平均Shannon信息指数(I)为1.176,变幅为0.143~1.908;观察杂合度(Ho)为0.977,范围为0.936~1.000;期望杂合度(He)为0.439,范围为0.179~0.937;固定指数(Fis)的范围为0.882~1.000;基因流(Nm)的范围为0~0.0157。聚类分析表明,在遗传相似系数为0.805处,东南亚水稻亲本被分为6大类,同一国家大多数品种聚为一类。相对于普通分子标记,功能基因标记的平均等位基因数不高,其遗传多样性参数也低于普通分子标记,东南亚各国水稻品种间的亲缘关系较近,遗传多样性程度较低。研究结果为水稻育种亲本选配、新种质资源的创制以及杂种优势利用等提供了科学依据。
利用RFLP、SSR、AFLP和RAPD标记分析玉米自交系遗传多样性的比较研究
采用表型和分子标记聚类研究杂交籼稻亲本的遗传多样性
以41份杂交籼稻骨干亲本和部分新育成的亲本为试验材料,采用表型性状和SSR分子标记2种聚类分析方法对杂交籼稻亲本的类群划分进行了比较研究,表型聚类以15个表型性状为依据,将供试材料划分为早、中熟和中、晚熟两大类群、6个亚群。早、中熟类群包含15个保持系、4个早熟恢复系和2个温敏核雄性不育系;中、晚熟类群包括16个恢复系和4个中、晚熟保持系。利用SSR分子标记将供试材料划分为保持系和恢复系两大类群、7个亚群。保持系群包括全部19个保持系、2个温敏核雄性不育系,恢复系群则包含全部20个恢复系,分类结果和系谱分析基本吻合。结合杂交籼稻育种实践,判断分子标记可能是研究亲本遗传多样性的一种较好方法。
中国小麦微核心种质及地方品种籽粒休眠特性的分子标记鉴定
DOI:10.3724/SP.J.1006.2010.01649
[本文引用: 1]

为探索我国小麦微核心种质及地方品种籽粒休眠的遗传基础,利用已报道的4个3AS上的SSR标记(Xbarc57、Xbarc294、Xbarc310和Xbarc321)和1个3BL上的Viviparous-1基因标记Vp1-b2对107份我国小麦微核心种质及31份地方品种进行籽粒休眠的分子标记鉴定。结果表明,5个分子标记在试验材料中表现出丰富的等位变异,具有5~6种等位类型,与籽粒萌芽指数(GI)密切相关。根据一般线性模型分析结果,各位点的等位变异显著影响籽粒休眠,其中Vp1-b2和Xbarc294对籽粒休眠作用较其他标记大,可分别解释65.8%和61.2% 的表型变异;其次是Xbarc310 (56.3%)和Xbarc57 (55.8%),最小的是Xbarc294(53.3%)。而5个标记联合可解释95.9% 的性状变异,其次是Vp1-b2和Xbarc294的组合(89.1%),解释变异最小的标记组合是 Vp1-b2和Xbarc321 (79.4%)。5个分子标记即可解释籽粒休眠的绝大部分表型变异,说明我国小麦微核心种质及地方品种籽粒休眠特性受3AS和3BL上的2个主效基因控制。
长江流域主要常规双季早籼稻的遗传相似性分析及指纹图谱构建
DOI:10.16819/j.1001-7216.2017.6117
[本文引用: 1]

目的 构建常规早稻品种的指纹图谱以及分析其遗传相似性,为早稻品种鉴定、育种者有效选配亲本提供参考依据。方法 以2000年以来长江流域双季稻区通过省级以上审定的常规早稻品种为材料,利用50对多态性高,稳定性好,且均匀分布于水稻12条染色体的SSR引物,建立常规早稻的SSR指纹图谱。利用NTSYS PC Version 2.10e 软件、UPGMA法进行聚类分析。结果 50对引物共检测到多态性位点154个,每对引物检测到的等位基因数为2~6个,平均3.08个;引物多态信息含量(PIC)值为0.03~0.75,平均值为0.36。62份材料的遗传相似系数变化范围为0.66~1,并且在相似系数为0.73处可分为浙江省内品种及省外品种2组,各组间差异不大。结论 结合系谱关系发现,本研究中所用早稻品种的遗传背景较为狭窄。
Genetic structure and diversity of indigenous rice (Oryza sativa) varieties in the Eastern Himalayan region of Northeast India
DOI:10.1186/2193-1801-2-228
PMID:23741655
[本文引用: 1]

The Eastern Himalayan region of Northeast (NE) India is home to a large number of indigenous rice varieties, which may serve as a valuable genetic resource for future crop improvement to meet the ever-increasing demand for food production. However, these varieties are rapidly being lost due to changes in land-use and agricultural practices, which favor agronomically improved varieties. A detailed understanding of the genetic structure and diversity of indigenous rice varieties is crucial for efficient utilization of rice genetic resources and for developing suitable conservation strategies. To explore the genetic structure and diversity of rice varieties in NE India, we genotyped 300 individuals of 24 indigenous rice varieties representing sali, boro, jum and glutinous types, 5 agronomically improved varieties, and one wild rice species (O. rufipogon) using seven SSR markers. A total of 85 alleles and a very high level of gene diversity (0.776) were detected among the indigenous rice varieties of the region. Considerable level of genetic variation was found within indigenous varieties whereas improved varieties were monoporphic across all loci. The comparison of genetic diversity among different types of rice revealed that sali type possessed the highest gene diversity (0.747) followed by jum (0.627), glutinous (0.602) and boro (0.596) types of indigenous rice varieties, while the lowest diversity was detected in agronomically improved varieties (0.459). The AMOVA results showed that 66% of the variation was distributed among varieties indicating a very high level of genetic differentiation in rice varieties in the region. Two major genetically defined clusters corresponding to indica and japonica groups were detected in rice varieties of the region. Overall, traditionally cultivated indigenous rice varieties in NE India showed high levels of genetic diversity comparable to levels of genetic diversity reported from wild rice populations in various parts of the world. The efforts for conservation of rice germplasm in NE India should consider saving rice varieties representing different types with specific emphasis given to sali and jum types. The protection against the loss of vast genetic diversity found in indigenous rice varieties in NE India is crucial for maintaining future food security in the changing world.
Genetic structure and diversity in Oryza sativa L.
DOI:10.1534/genetics.104.035642
URL

The population structure of domesticated species is influenced by the natural history of the populations of predomesticated ancestors, as well as by the breeding system and complexity of the breeding practices exercised by humans. Within Oryza sativa, there is an ancient and well-established divergence between the two major subspecies, indica and japonica, but finer levels of genetic structure are suggested by the breeding history. In this study, a sample of 234 accessions of rice was genotyped at 169 nuclear SSRs and two chloroplast loci. The data were analyzed to resolve the genetic structure and to interpret the evolutionary relationships between groups. Five distinct groups were detected, corresponding to indica, aus, aromatic, temperate japonica, and tropical japonica rices. Nuclear and chloroplast data support a closer evolutionary relationship between the indica and the aus and among the tropical japonica, temperate japonica, and aromatic groups. Group differences can be explained through contrasting demographic histories. With the availability of rice genome sequence, coupled with a large collection of publicly available genetic resources, it is of interest to develop a population-based framework for the molecular analysis of diversity in O. sativa.
Population structure and genetic diversity in a rice core collection (Oryza sativa L.) investigated with SSR markers
DOI:10.1371/journal.pone.0027565 URL [本文引用: 1]
Genetic architecture of aluminum tolerance in rice (Oryza sativa) determined through genome- wide association analysis and QTL mapping
DOI:10.1371/journal.pgen.1002221 URL [本文引用: 1]
广西水稻地方品种耐冷性鉴定及相关分析
DOI:10.13430/j.cnki.jpgr.2016.06.002
[本文引用: 1]

对419份广西水稻地方品种初级核心种质进行芽期、苗期的耐冷性鉴定及相关分析,结果表明:广西水稻地方品种芽期、苗期耐冷性主要集中在7级和9级,总体耐冷性较弱。芽期、苗期强耐冷种质(1级)分别为24份和27份,占参试总数的5.73%和6.44%,其中10份种质芽期和苗期均表现强耐冷(1级)。芽期、苗期耐冷性呈极显著正相关(r=0.66)。在籼稻与粳稻、粘稻与糯稻间耐冷性存在显著差异,粳稻芽期、苗期耐冷性均显著高于籼稻;糯稻芽期耐冷性显著高于粘稻,但苗期耐冷性无差异。来自高寒山区稻作区的品种平均耐冷表现最强,芽期、苗期耐冷性显著高于桂南、桂北稻作区,但与桂中稻作区无差异。利用34个SSR标记与芽期、苗期耐冷性进行相关分析,在第7和第9染色体上,各鉴定出1个同时与芽期和苗期耐冷性相关联的位点。本研究为水稻芽、苗期耐冷育种提供新的抗源材料,并为水稻耐冷基因定位及机理研究奠定基础。
粳稻米碱消值的数量性状基因座检测
DOI:10.3724/SP.J.1006.2010.00115
[本文引用: 1]

利用碱消值差异显著的大粒粳稻DL115与小粒粳稻XL005杂交获得的200个单株F<sub>2</sub>群体为作图群体, 采用复合区间作图方法, 利用SSR标记进行了粳稻碱消值数量性状基因座的检测。结果表明, 在F<sub>2</sub>群体中碱消值呈正态连续分布, 表现为由多基因控制的数量性状。共检测到与碱消值相关的QTL 3个, qADV3、qADV5和qADV11, 分别位于第3、第5和第11染色体的RM14870~RM1284、RM3838~RM3351和RM1812~RM332区间, 对表型变异的解释率分别为6.5%、10.3%和8.1%。qADV5的增效等位基因来自碱消值较小的亲本XL005, qADV3和qADV11的增效等位基因来自碱消值较大的亲本DL115; 基因作用方式表现为显性或超显性。
Principal component analysis for assessment of genetic diversity in rainfed shallow lowland rice (Oryza sativa L)
玉米机械化籽粒收获组合鉴定与主成分分析
264份谷子主要育成品种(系)表型多样性综合评价
花生种质资源表型性状的综合评价及指标筛选
DOI:10.13430/j.cnki.jpgr.20180105001
[本文引用: 1]

分析花生种质资源表型性状的遗传变异规律,构建花生种质资源的综合评价体系,筛选最优的评价指标。本研究以40份花生种质资源的17个表型性状为研究对象,利用变异系数与Shannon-Weaver多样性指数对表型性状的遗传多样性进行分析,采用聚类分析、主成分分析以及逐步回归分析对花生种质资源进行了综合评价和鉴定指标的筛选。结果表明:17个表型性状的变异系数变化范围为4.15%-31.82%,油酸、亚油酸以及蔗糖含量的性状变异丰富,出仁率、粗脂肪及蛋白质的性状较稳定。多样性指数变化范围为1.39-2.06,主茎高、百仁重及蛋白质的性状分布比较均匀,油酸、亚油酸及棕榈酸的性状分级及分布较不均匀。聚类分析把40份花生种质资源分为了4个类群。主成分分析把17个表型性状归为5个主成分(累计贡献率80.41%,反映出17个表型性状的大部分信息),依次为花生籽粒含油量因子、籽粒含糖量因子及丰产性因子,以上因子可以较准确的评价花生种质。花生种质表型性状的综合评价由F值大小判定,F值均值为0.73,开农176的F值最高,阜花12号的F值最低。由逐步回归分析筛选出8个表型性状:单株鲜果重、百果重、出仁率、粗脂肪、蛋白质、棕榈酸、油酸和蔗糖含量。花生种质资源遗传多样性较丰富,综合评价F值可以为花生种质资源评价提供参考,筛选的8个表型性状可以作为花生种质资源性状评价指标。
60份不同来源粳稻种质资源表型性状的多样性分析及综合评价
DOI:10.3969/j.issn.1006-8082.2022.06.015
[本文引用: 1]

为更好选择和利用优势亲本,提高水稻新品种选育效率,以来自福建、东北地区和宁夏的60份水稻种质为材料,通过变异系数、遗传多样性指数、聚类分析、主成分分析、逐步回归分析等方法对水稻18个主要表型性状的多样性进行评价。结果表明,18个表型性状的变异系数在1.10%~63.40%之间,其中黄粒米的变异系数最大(63.40%),整精米率、垩白粒率、垩白度、不完善粒等稻米外观品质变异系数次之,均在34.00%以上,出糙率和生育期的变异系数较小,分别是1.10%和2.94%;18个性状的表型多样性指数为1.74~2.10,其中生育期的多样性指数最低,小区产量的多样性指数最高;按照来源对60份稻种资源表型多样性指数进行分析,各地区稻种资源的表型多样性指数变异较大,其中福建的变异幅度最大(1.06~2.10)、东北次之(1.50~2.09)、宁夏变异范围最小(1.51~2.01)。参试水稻资源在遗传距离为1.03时分4类,明确了各类资源的特征特性;基于主成分分析的综合D值,对种质资源进行排序,筛选的综合得分最高的前10名种质;同时利用主成分分析的D值与逐步回归分析,构建了水稻资源评价方程,该方程的构建为水稻资源综合评价、筛选提供了依据。
基于非线性主成分分析的绿色超级稻品种综合评价
DOI:10.3724/SP.J.1006.2019.82057
[本文引用: 1]

应用绿色超级稻被认为是推动水稻生产可持续发展的重要途径之一, 已成为全球水稻育种的主要目标。目前关于绿色超级稻品种综合评价的研究鲜有报道。本文围绕“少打农药、少施化肥、节水抗旱、优质高产”的理念, 从技术性、经济性、生态性和社会性4个维度构建了绿色超级稻品种综合评价指标体系, 为水稻及其他作物品种的综合评价、品种选育及推广应用提供了有益的研究思路。在此基础上引入一种非线性主成分分析法——对数主成分分析, 利用大田试验数据及不同评价方法的对比分析表明, 对数主成分分析法符合绿色超级稻的育种理念, 具有较强的合理性, 可作为一种有效的水稻品种综合评价方法。