Molecular regulation of seed development and strategies for engineering seed size in crop plants
... Functional genes related to seed size/weight in plants
Table 1 基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| 激素信号转导Hormone signal transduction |
| KLU | Arabidopsis | AT1G13710 | Cytochrome P450 | 5 | [20] |
| SOB7 | Arabidopsis | AT1G17060 | Cytochrome p450 72C1 | 13 | [21] |
| AHK3 | Arabidopsis | AT1G27320 | Histidine kinase 3 | 2 | [20] |
| CKX5 | Arabidopsis | AT1G75450 | Cytokinin oxidase 5 | 2 | [22] |
| AHK4 | Arabidopsis | AT2G01830 | Histidine kinase: cytokinin-binding receptor | 5 | [20] |
| DET2 | Arabidopsis | AT2G38050 | Brassinolide biosynthetic | 2 | [20] |
| CKX1 | Arabidopsis | AT2G41510 | Cytokinin oxidase/dehydrogenase 1 | 2 | [22] |
| EOD3 | Arabidopsis | AT2G46660 | Cytochrome P450 | 3 | [21] |
| DWF4 | Arabidopsis | AT3G50660 | Cytochrome P450 superfamily protein | 3 | [5] |
| CYP78A9 | Arabidopsis | AT3G61880 | Cytochrome P450 78a9 | 3 | [21] |
| AP2 | Arabidopsis | AT4G36920 | Integrase-type DNA-binding superfamily protein | 4 | [7] |
| ATMYB56 | Arabidopsis | AT5G17800 | Myb domain protein 56 | 2 | [22] |
| AGG3 | Arabidopsis | AT5G20635 | Atypical heterotrimeric G-protein gamma-subunit | 4 | [23] |
| AHK2 | Arabidopsis | AT5G35750 | Histidine kinase AHK2 | 2 | [20] |
| ABA2 | Arabidopsis | AT1G52340 | Xanthoxin dehydrogenase | 2 | [21] |
| ABI5 | Arabidopsis | AT2G36270 | Basic-leucine zipper (bZIP) transcription factor family protein | 3 | [21] |
| BRI1 | Arabidopsis | AT4G39400 | Protein BRASSINOSTEROID INSENSITIVE 1 | 2 | [21] |
| ARF2 | Arabidopsis | AT5G62000 | Auxin response factor 2 | 4 | [5] |
| DWARF 61 | Rice | OS01G0718300 | Receptor serine/threonine kinase | 2 | [23] |
| OsBZR1 | Rice | OS07G0580500 | Brassinosteroid (BR) regulated growth response | 6 | [21] |
| GSK2 | Rice | OS05G0207500 | GSK3/SHAGGY-like kinase | 1 | [21] |
| BG1 | Rice | Os03g0175800 | Positive regulator of auxin response and transport | 1 | [21] |
| DWARF 11 | Rice | OS04G0469800 | Brassinosteroid (BR) biosynthesis | 1 | [21] |
| GE | Rice | OS07G0603700 | Cytochrome P450 78A5 | 5 | [23] |
| 泛素代谢途径Ubiquitin pathway |
| GW2 | Rice | OS02G0244100 | RING-type E3 ubiquitin ligase | 2 | [8] |
| UBP15 | Arabidopsis | AT1G17110 | Ubiquitin-specific protease 15 | 2 | [24] |
| DA1 | Arabidopsis | AT1G19270 | Ubiquitin receptors | 2 | [25] |
| DA2 | Arabidopsis | AT1G78420 | E3 ubiquitin-protein ligase DA2 | 2 | [26] |
| EOD1 | Arabidopsis | AT3G63530 | E3 ubiquitin ligase | 2 | [21] |
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
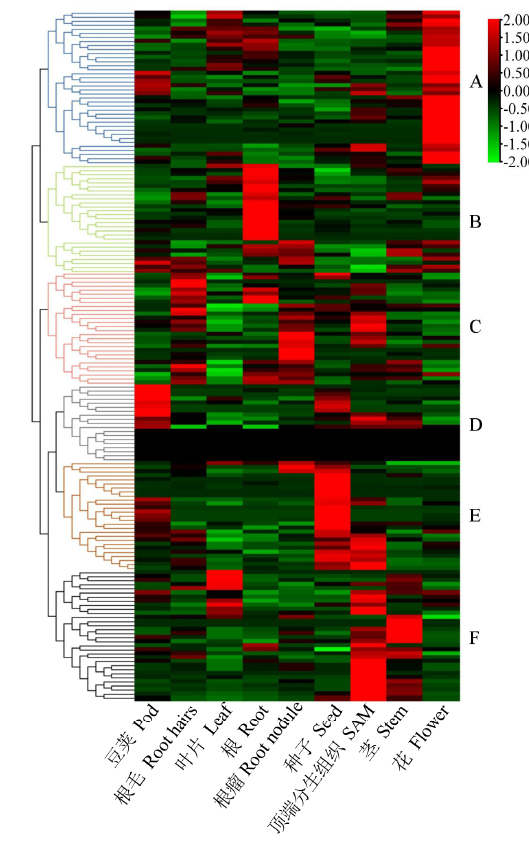
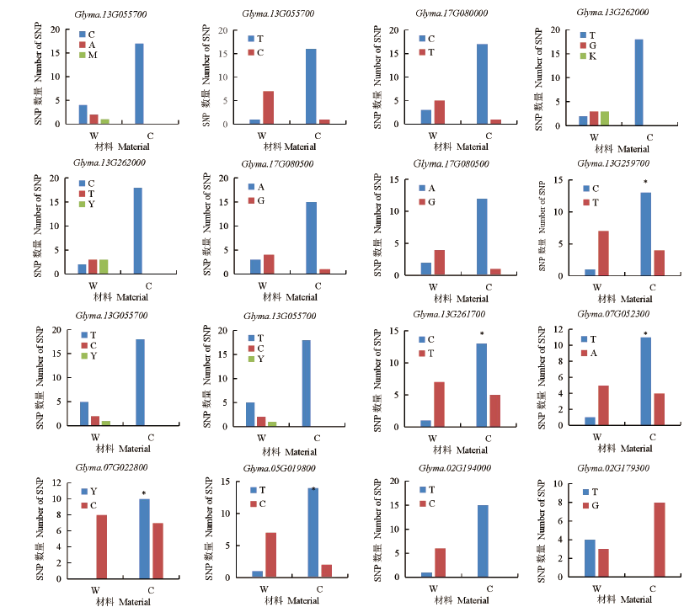
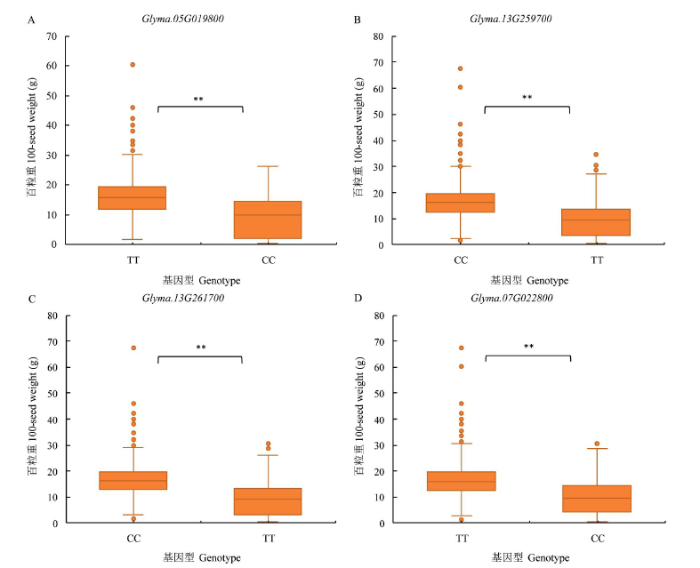
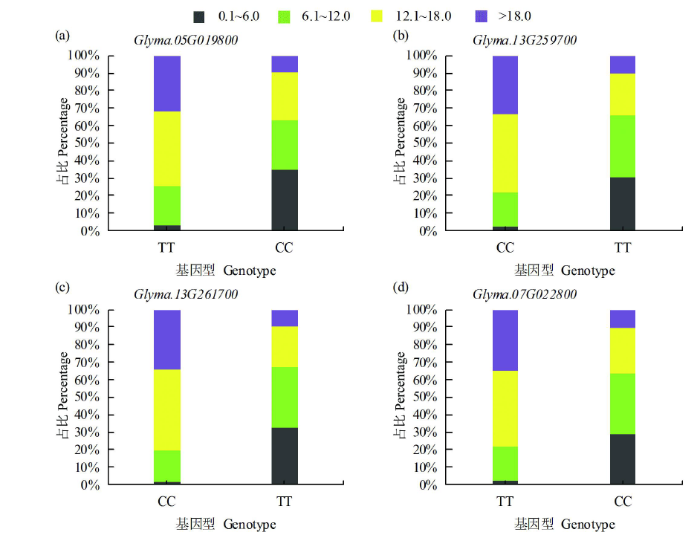
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| DWF4 | Arabidopsis | AT3G50660 | Cytochrome P450 superfamily protein | 3 | [5] |
| CYP78A9 | Arabidopsis | AT3G61880 | Cytochrome P450 78a9 | 3 | [21] |
| AP2 | Arabidopsis | AT4G36920 | Integrase-type DNA-binding superfamily protein | 4 | [7] |
| ATMYB56 | Arabidopsis | AT5G17800 | Myb domain protein 56 | 2 | [22] |
| AGG3 | Arabidopsis | AT5G20635 | Atypical heterotrimeric G-protein gamma-subunit | 4 | [23] |
| AHK2 | Arabidopsis | AT5G35750 | Histidine kinase AHK2 | 2 | [20] |
| ABA2 | Arabidopsis | AT1G52340 | Xanthoxin dehydrogenase | 2 | [21] |
| ABI5 | Arabidopsis | AT2G36270 | Basic-leucine zipper (bZIP) transcription factor family protein | 3 | [21] |
| BRI1 | Arabidopsis | AT4G39400 | Protein BRASSINOSTEROID INSENSITIVE 1 | 2 | [21] |
| ARF2 | Arabidopsis | AT5G62000 | Auxin response factor 2 | 4 | [5] |
| DWARF 61 | Rice | OS01G0718300 | Receptor serine/threonine kinase | 2 | [23] |
| OsBZR1 | Rice | OS07G0580500 | Brassinosteroid (BR) regulated growth response | 6 | [21] |
| GSK2 | Rice | OS05G0207500 | GSK3/SHAGGY-like kinase | 1 | [21] |
| BG1 | Rice | Os03g0175800 | Positive regulator of auxin response and transport | 1 | [21] |
| DWARF 11 | Rice | OS04G0469800 | Brassinosteroid (BR) biosynthesis | 1 | [21] |
| GE | Rice | OS07G0603700 | Cytochrome P450 78A5 | 5 | [23] |
| 泛素代谢途径Ubiquitin pathway |
| GW2 | Rice | OS02G0244100 | RING-type E3 ubiquitin ligase | 2 | [8] |
| UBP15 | Arabidopsis | AT1G17110 | Ubiquitin-specific protease 15 | 2 | [24] |
| DA1 | Arabidopsis | AT1G19270 | Ubiquitin receptors | 2 | [25] |
| DA2 | Arabidopsis | AT1G78420 | E3 ubiquitin-protein ligase DA2 | 2 | [26] |
| EOD1 | Arabidopsis | AT3G63530 | E3 ubiquitin ligase | 2 | [21] |
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| AP2 | Arabidopsis | AT4G36920 | Integrase-type DNA-binding superfamily protein | 4 | [7] |
| ATMYB56 | Arabidopsis | AT5G17800 | Myb domain protein 56 | 2 | [22] |
| AGG3 | Arabidopsis | AT5G20635 | Atypical heterotrimeric G-protein gamma-subunit | 4 | [23] |
| AHK2 | Arabidopsis | AT5G35750 | Histidine kinase AHK2 | 2 | [20] |
| ABA2 | Arabidopsis | AT1G52340 | Xanthoxin dehydrogenase | 2 | [21] |
| ABI5 | Arabidopsis | AT2G36270 | Basic-leucine zipper (bZIP) transcription factor family protein | 3 | [21] |
| BRI1 | Arabidopsis | AT4G39400 | Protein BRASSINOSTEROID INSENSITIVE 1 | 2 | [21] |
| ARF2 | Arabidopsis | AT5G62000 | Auxin response factor 2 | 4 | [5] |
| DWARF 61 | Rice | OS01G0718300 | Receptor serine/threonine kinase | 2 | [23] |
| OsBZR1 | Rice | OS07G0580500 | Brassinosteroid (BR) regulated growth response | 6 | [21] |
| GSK2 | Rice | OS05G0207500 | GSK3/SHAGGY-like kinase | 1 | [21] |
| BG1 | Rice | Os03g0175800 | Positive regulator of auxin response and transport | 1 | [21] |
| DWARF 11 | Rice | OS04G0469800 | Brassinosteroid (BR) biosynthesis | 1 | [21] |
| GE | Rice | OS07G0603700 | Cytochrome P450 78A5 | 5 | [23] |
| 泛素代谢途径Ubiquitin pathway |
| GW2 | Rice | OS02G0244100 | RING-type E3 ubiquitin ligase | 2 | [8] |
| UBP15 | Arabidopsis | AT1G17110 | Ubiquitin-specific protease 15 | 2 | [24] |
| DA1 | Arabidopsis | AT1G19270 | Ubiquitin receptors | 2 | [25] |
| DA2 | Arabidopsis | AT1G78420 | E3 ubiquitin-protein ligase DA2 | 2 | [26] |
| EOD1 | Arabidopsis | AT3G63530 | E3 ubiquitin ligase | 2 | [21] |
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| ABI5 | Arabidopsis | AT2G36270 | Basic-leucine zipper (bZIP) transcription factor family protein | 3 | [21] |
| BRI1 | Arabidopsis | AT4G39400 | Protein BRASSINOSTEROID INSENSITIVE 1 | 2 | [21] |
| ARF2 | Arabidopsis | AT5G62000 | Auxin response factor 2 | 4 | [5] |
| DWARF 61 | Rice | OS01G0718300 | Receptor serine/threonine kinase | 2 | [23] |
| OsBZR1 | Rice | OS07G0580500 | Brassinosteroid (BR) regulated growth response | 6 | [21] |
| GSK2 | Rice | OS05G0207500 | GSK3/SHAGGY-like kinase | 1 | [21] |
| BG1 | Rice | Os03g0175800 | Positive regulator of auxin response and transport | 1 | [21] |
| DWARF 11 | Rice | OS04G0469800 | Brassinosteroid (BR) biosynthesis | 1 | [21] |
| GE | Rice | OS07G0603700 | Cytochrome P450 78A5 | 5 | [23] |
| 泛素代谢途径Ubiquitin pathway |
| GW2 | Rice | OS02G0244100 | RING-type E3 ubiquitin ligase | 2 | [8] |
| UBP15 | Arabidopsis | AT1G17110 | Ubiquitin-specific protease 15 | 2 | [24] |
| DA1 | Arabidopsis | AT1G19270 | Ubiquitin receptors | 2 | [25] |
| DA2 | Arabidopsis | AT1G78420 | E3 ubiquitin-protein ligase DA2 | 2 | [26] |
| EOD1 | Arabidopsis | AT3G63530 | E3 ubiquitin ligase | 2 | [21] |
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| BRI1 | Arabidopsis | AT4G39400 | Protein BRASSINOSTEROID INSENSITIVE 1 | 2 | [21] |
| ARF2 | Arabidopsis | AT5G62000 | Auxin response factor 2 | 4 | [5] |
| DWARF 61 | Rice | OS01G0718300 | Receptor serine/threonine kinase | 2 | [23] |
| OsBZR1 | Rice | OS07G0580500 | Brassinosteroid (BR) regulated growth response | 6 | [21] |
| GSK2 | Rice | OS05G0207500 | GSK3/SHAGGY-like kinase | 1 | [21] |
| BG1 | Rice | Os03g0175800 | Positive regulator of auxin response and transport | 1 | [21] |
| DWARF 11 | Rice | OS04G0469800 | Brassinosteroid (BR) biosynthesis | 1 | [21] |
| GE | Rice | OS07G0603700 | Cytochrome P450 78A5 | 5 | [23] |
| 泛素代谢途径Ubiquitin pathway |
| GW2 | Rice | OS02G0244100 | RING-type E3 ubiquitin ligase | 2 | [8] |
| UBP15 | Arabidopsis | AT1G17110 | Ubiquitin-specific protease 15 | 2 | [24] |
| DA1 | Arabidopsis | AT1G19270 | Ubiquitin receptors | 2 | [25] |
| DA2 | Arabidopsis | AT1G78420 | E3 ubiquitin-protein ligase DA2 | 2 | [26] |
| EOD1 | Arabidopsis | AT3G63530 | E3 ubiquitin ligase | 2 | [21] |
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| ARF2 | Arabidopsis | AT5G62000 | Auxin response factor 2 | 4 | [5] |
| DWARF 61 | Rice | OS01G0718300 | Receptor serine/threonine kinase | 2 | [23] |
| OsBZR1 | Rice | OS07G0580500 | Brassinosteroid (BR) regulated growth response | 6 | [21] |
| GSK2 | Rice | OS05G0207500 | GSK3/SHAGGY-like kinase | 1 | [21] |
| BG1 | Rice | Os03g0175800 | Positive regulator of auxin response and transport | 1 | [21] |
| DWARF 11 | Rice | OS04G0469800 | Brassinosteroid (BR) biosynthesis | 1 | [21] |
| GE | Rice | OS07G0603700 | Cytochrome P450 78A5 | 5 | [23] |
| 泛素代谢途径Ubiquitin pathway |
| GW2 | Rice | OS02G0244100 | RING-type E3 ubiquitin ligase | 2 | [8] |
| UBP15 | Arabidopsis | AT1G17110 | Ubiquitin-specific protease 15 | 2 | [24] |
| DA1 | Arabidopsis | AT1G19270 | Ubiquitin receptors | 2 | [25] |
| DA2 | Arabidopsis | AT1G78420 | E3 ubiquitin-protein ligase DA2 | 2 | [26] |
| EOD1 | Arabidopsis | AT3G63530 | E3 ubiquitin ligase | 2 | [21] |
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| GSK2 | Rice | OS05G0207500 | GSK3/SHAGGY-like kinase | 1 | [21] |
| BG1 | Rice | Os03g0175800 | Positive regulator of auxin response and transport | 1 | [21] |
| DWARF 11 | Rice | OS04G0469800 | Brassinosteroid (BR) biosynthesis | 1 | [21] |
| GE | Rice | OS07G0603700 | Cytochrome P450 78A5 | 5 | [23] |
| 泛素代谢途径Ubiquitin pathway |
| GW2 | Rice | OS02G0244100 | RING-type E3 ubiquitin ligase | 2 | [8] |
| UBP15 | Arabidopsis | AT1G17110 | Ubiquitin-specific protease 15 | 2 | [24] |
| DA1 | Arabidopsis | AT1G19270 | Ubiquitin receptors | 2 | [25] |
| DA2 | Arabidopsis | AT1G78420 | E3 ubiquitin-protein ligase DA2 | 2 | [26] |
| EOD1 | Arabidopsis | AT3G63530 | E3 ubiquitin ligase | 2 | [21] |
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| BG1 | Rice | Os03g0175800 | Positive regulator of auxin response and transport | 1 | [21] |
| DWARF 11 | Rice | OS04G0469800 | Brassinosteroid (BR) biosynthesis | 1 | [21] |
| GE | Rice | OS07G0603700 | Cytochrome P450 78A5 | 5 | [23] |
| 泛素代谢途径Ubiquitin pathway |
| GW2 | Rice | OS02G0244100 | RING-type E3 ubiquitin ligase | 2 | [8] |
| UBP15 | Arabidopsis | AT1G17110 | Ubiquitin-specific protease 15 | 2 | [24] |
| DA1 | Arabidopsis | AT1G19270 | Ubiquitin receptors | 2 | [25] |
| DA2 | Arabidopsis | AT1G78420 | E3 ubiquitin-protein ligase DA2 | 2 | [26] |
| EOD1 | Arabidopsis | AT3G63530 | E3 ubiquitin ligase | 2 | [21] |
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| DWARF 11 | Rice | OS04G0469800 | Brassinosteroid (BR) biosynthesis | 1 | [21] |
| GE | Rice | OS07G0603700 | Cytochrome P450 78A5 | 5 | [23] |
| 泛素代谢途径Ubiquitin pathway |
| GW2 | Rice | OS02G0244100 | RING-type E3 ubiquitin ligase | 2 | [8] |
| UBP15 | Arabidopsis | AT1G17110 | Ubiquitin-specific protease 15 | 2 | [24] |
| DA1 | Arabidopsis | AT1G19270 | Ubiquitin receptors | 2 | [25] |
| DA2 | Arabidopsis | AT1G78420 | E3 ubiquitin-protein ligase DA2 | 2 | [26] |
| EOD1 | Arabidopsis | AT3G63530 | E3 ubiquitin ligase | 2 | [21] |
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| GE | Rice | OS07G0603700 | Cytochrome P450 78A5 | 5 | [23] |
| 泛素代谢途径Ubiquitin pathway |
| GW2 | Rice | OS02G0244100 | RING-type E3 ubiquitin ligase | 2 | [8] |
| UBP15 | Arabidopsis | AT1G17110 | Ubiquitin-specific protease 15 | 2 | [24] |
| DA1 | Arabidopsis | AT1G19270 | Ubiquitin receptors | 2 | [25] |
| DA2 | Arabidopsis | AT1G78420 | E3 ubiquitin-protein ligase DA2 | 2 | [26] |
| EOD1 | Arabidopsis | AT3G63530 | E3 ubiquitin ligase | 2 | [21] |
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| DAR1 | Arabidopsis | AT4G36860 | Ubiquitin binding protein | 6 | [23] |
| 其他Others |
| SAMBA | Arabidopsis | AT1G32310 | Valine-tRNA ligase | 2 | [23] |
| MINI3 | Arabidopsis | AT1G55600 | Member of WRKY Transcription Factor | 2 | [2] |
| IKU1 | Arabidopsis | AT2G35230 | VQ motif-containing protein | 5 | [20] |
| TTG2 | Arabidopsis | AT2G37260 | WRKY family transcription factor | 2 | [20] |
| SOD7 | Arabidopsis | AT3G11580 | AP2/B3-like transcriptional factor | 4 | [21] |
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| IKU2 | Arabidopsis | AT3G19700 | Leucine-rich repeat protein kinase | 1 | [20] |
| FER | Arabidopsis | AT3G51550 | Malectin/receptor-like protein kinase | 2 | [21] |
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| STK | Arabidopsis | AT4G09960 | MADS box transcription factor | 2 | [22] |
基因名称
Gene name | 物种
Species | 基因编号
Gene ID | 生物学功能
Biological function | 大豆中基因拷贝数
Copy number in soybean | 参考文献
Reference |
| RPT2A | Arabidopsis | AT4G29040 | Regulatory particle AAA-ATPase 2A | 4 | [23] |
| ANT | Arabidopsis | AT4G37750 | Integrase-type DNA-binding superfamily protein | 8 | [20] |
| DPA4 | Arabidopsis | AT5G06250 | AP2/B3-like transcriptional factor | 4 | [21] |
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| MET1 | Arabidopsis | AT5G49160 | Methyltransferase 1 | 2 | [23] |
| AGL62 | Arabidopsis | AT5G60440 | AGAMOUS-like 62 | 24 | [20] |
| SHB1 | Arabidopsis | At4G25350 | Acts in cryptochrome signaling | 1 | [20] |
| GS2 | Rice | Os02G0701300 | Growth-regulating factor 4-like | 1 | [21] |
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| SMG1 | Rice | OS02G0787300 | Mitogen-activated protein kinase kinase 5 | 2 | [23] |
| GS3 | Rice | OS03G0407400 | Keratin-associated protein 5-5 | 4 | [21] |
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| qGL3 | Rice | Os03G0646900 | Serine/threonine phosphatase | 1 | [21] |
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...
... [
21]
| RGB1 | Rice | OS03G0669100 | Deoxyuridine 5'-triphosphate nucleotidohydrolase-like | 2 | [23] |
| OsGIF1 | Rice | OS03G0733600 | GRF1-interacting factor 1 | 4 | [23] |
| GS5 | Rice | OS05G0158500 | Serine carboxypeptidase-like 26 | 3 | [23] |
| RGA1 | Rice | OS05G0333200 | Guanine nucleotide-binding protein alpha-1 subunit | 4 | [23] |
| OsMAPK6 | Rice | OS06G0154500 | Mitogen-activated protein kinase 1-like | 2 | [27] |
| TGW6 | Rice | OS06G0623700 | Protein STRICTOSIDINE SYNTHASE-LIKE 10 | 6 | [28] |
| GW6a | Rice | OS06G0650300 | Probable N-acetyltransferase HLS1 | 2 | [23] |
| GLW7 | Rice | Os07G0505200 | Plant-specific transcription factor | 1 | [23] |
| GW7 | Rice | OS07G0603300 | Protein LONGIFOLIA 1 | 8 | [29] |
| GW8 | Rice | OS08G0531600 | Squamosa promoter binding like protein 16 | 2 | [30] |
| DEP1 | Rice | OS09G0441900 | Keratin-associated protein 5-5 | 4 | [31] |
2.1.2 大豆百粒重相关基因的全基因组检索 基于序列相似和结构域相同的原则,查找水稻和拟南芥中与粒重相关的59个基因在大豆中的同源基因,共获得了175个基因(表2),由表2可知,其中174个基因分布于大豆20条染色体上,1个基因位于基因组的Scaffold上,这些基因在10号染色体上分布最多(22个),12号染色体上最少(2个),其他染色体上基因数目在3~13之间.从代谢途径来看,泛素代谢途径相关基因主要分布在1号、2号和10~17号染色体上;激素信号转导途径相关基因在除10号、12号、18号和20号染色体的其他染色体上均有分布.由表1可知,在59个调控植物籽粒大小/粒重的基因中,SHB1、GS2、BG1、GL3和GLW7基因在大豆中没有找到同源基因;IKU2、D11和GSK2基因在大豆中为单拷贝,其他基因均为多拷贝. ...